5.Ggplot
GGplot2: Paquete para hacer gráficos
Este paquete está enfocado en programar gráficas.
- Basado en el “Grammar of graphics”.
- La idea general es poder editar cada componente de un gráfico.
- Cada componente tiene su nombre y argumentos.
- “Mapear” significa usar cierta variable como un componente del gráfico.
- Parte del tidyverse así que funciona con la misma sintáxis.
Ventajas:
- 100 % editable.
- Visualmente más estética que los gráficos de R base.
- Permite crear prácticamente cualquier tipo de gráfica.
- Varios paquetes usan como base ggplot2 para generar sus propios gráficos.
Ejemplos de algunos tipos de gráficos
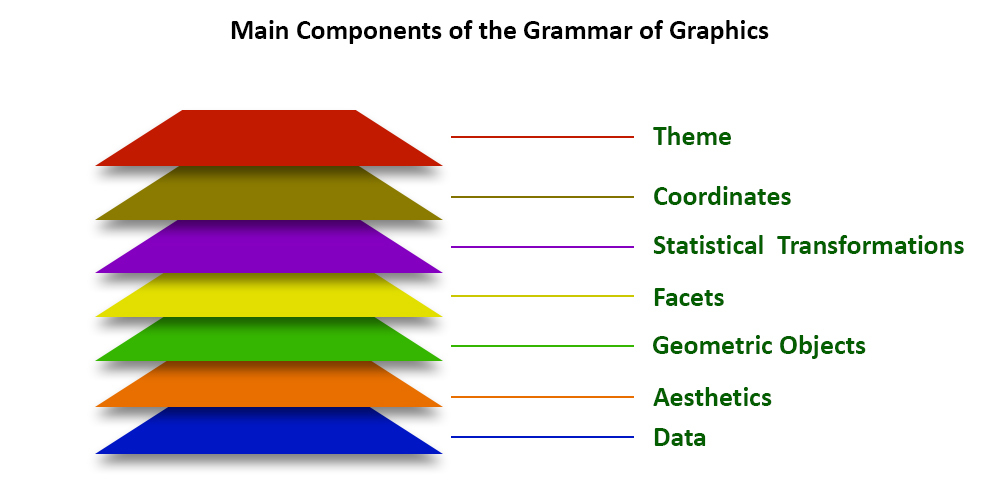
Los gráficos de ggplot normalmente siguen la siguiente estructura:
- Datos.
- Mapeo de variables estéticas
aes. - Adición de capas.
Como funciona ggplot2 es como si fueran capas similares a como se manejan imágenes en Photoshop o GIMP.
Esquema de cómo se crean las gráficas de ggplot.
Guía para saber qué parámetros modificar de un gráfico en ggplot: https://ggplot2tor.com/theme/.
Tipos de gráficos
Leer mismos datos
datos <- read_excel("INFyS_2015_2020_Michoacan_de_Ocampo_lHwLKIM.xlsx",
sheet = "Arbolado")Warning: Expecting numeric in BW19313 / R19313C75: got 'NULL'Warning: Expecting numeric in BX19313 / R19313C76: got 'NULL'# Preprocesamiento limpieza de datos
datos <- datos |>
mutate(across(c(AlturaTotal_C3, DiametroNormal_C3), ~ifelse(.x >= 99999, NA, .x))) |>
# Eliminar NA
drop_na(AlturaTotal_C3, DiametroNormal_C3) |>
# Seleccionar columnas de interés
select(IdConglomerado,DESCRIP_S7_C3,AlturaTotal_C3, DiametroNormal_C3, biomasa_kg_C3, Anio_C3, CVEECON1_C3) |>
# Renombrar columnas
rename("ParcelaId" = "IdConglomerado",
"TipoVeg" = "DESCRIP_S7_C3",
"Altura" = "AlturaTotal_C3",
"DAP" = "DiametroNormal_C3",
"Biomasa" = "biomasa_kg_C3",
"Anio" = "Anio_C3",
"Ecorregion" = "CVEECON1_C3") Generar base del gráfico
La primera parte genera el espacio o la base del gráfico.
datos |>
ggplot(aes(x = DAP,
y = Biomasa)) 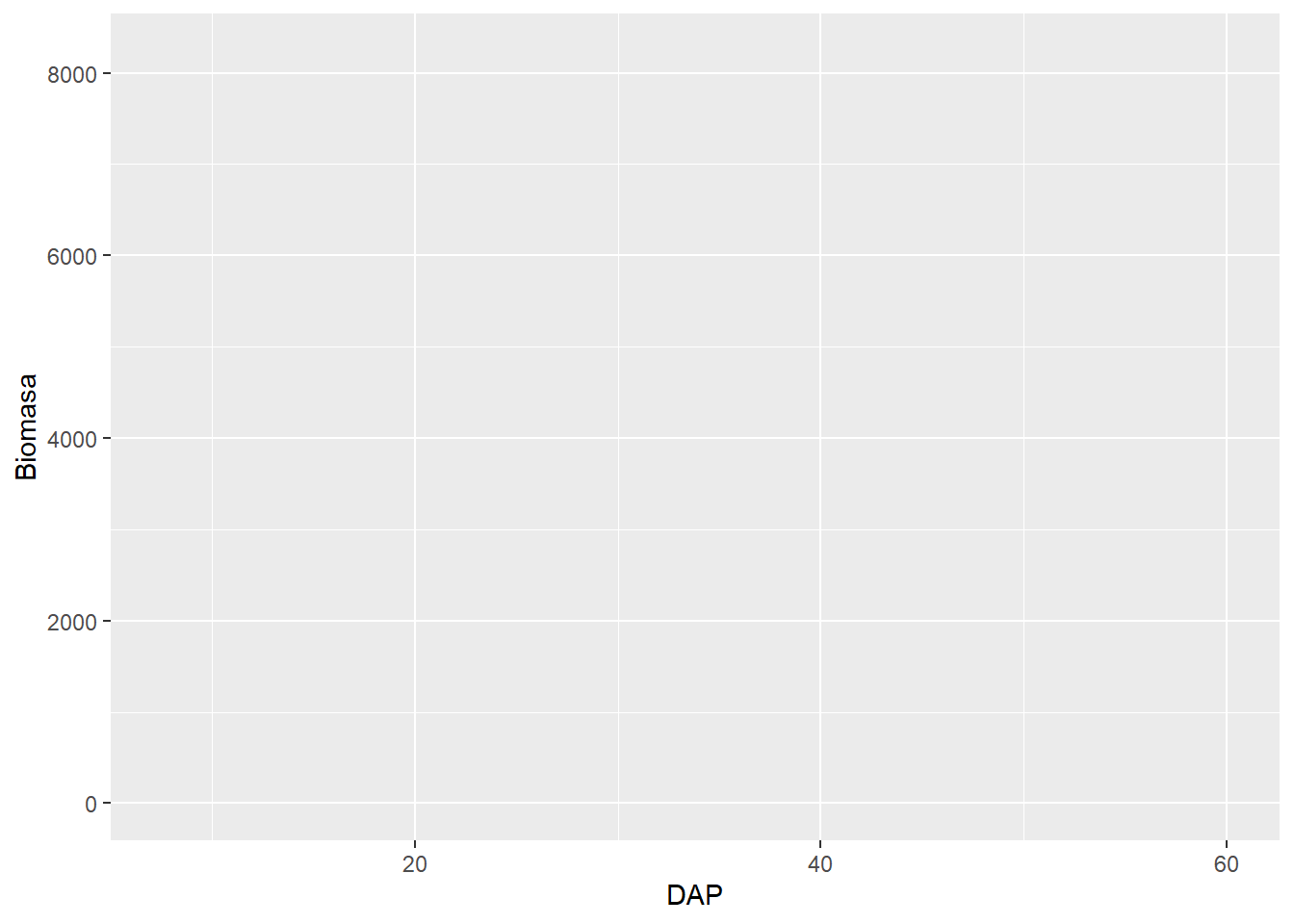
Después se define el estilo de gráfico que se desea.
Para agregar más capas a nuestro gráfico, dentro de ggplot siempre se usa + para agregar alguna capa o modificar el tema.
Todos los tipos de gráficas empiezan con geom_.
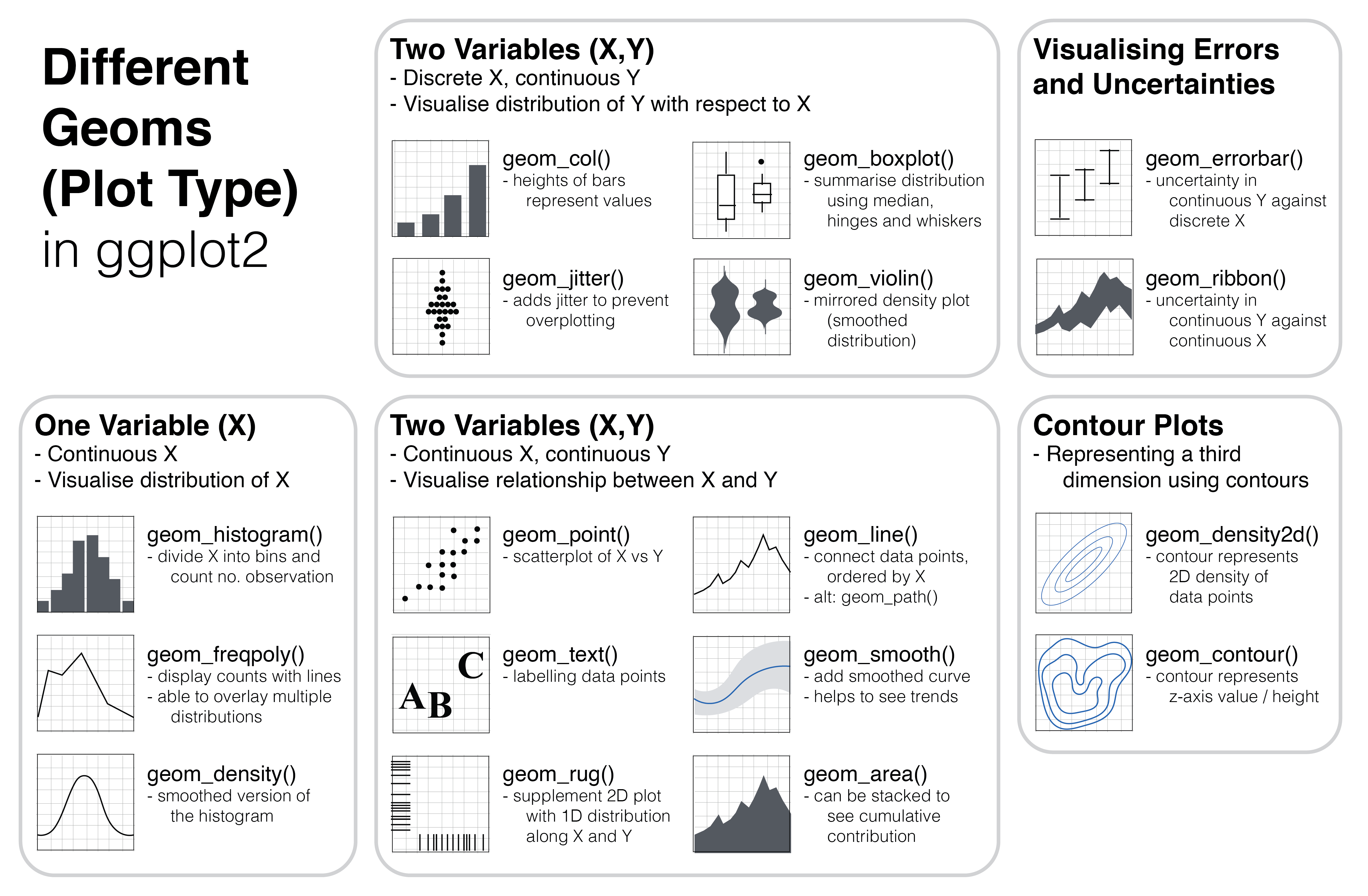
Scatterplot
datos |>
ggplot(aes(x = DAP,
y = Biomasa)) +
geom_point()
Las opciones básicas de tipos de gráficos son:
- geom_point.
- geom_area.
- geom_bar (frecuencias).
- geom_col (alguna otra variable).
- geom_boxplot.
- geom_errorbar
- geom_density.
- geom_histogram.
- geom_line.
- geom_smooth.
- geom_line.
Aunque hay muchas más, veamos algunos ejemplos.
Line
datos |>
ggplot(aes(x = DAP,
y = Biomasa)) +
geom_line()
Bar
La variable del eje Y corresponde a la frecuencia de la variable indicada como x.
datos |>
ggplot(aes(x = TipoVeg)) +
geom_bar()
Column
La variable del eje Y corresponde a otra variable, distinta de la del eje X.
datos |>
group_by(TipoVeg, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col()
Boxplot
datos |>
ggplot(aes(x = TipoVeg,
y = DAP)) +
geom_boxplot()
Histograma
datos |>
ggplot(aes(x = DAP)) +
geom_histogram()`stat_bin()` using `bins = 30`. Pick better value with `binwidth`.
Se pueden combinar varios.
datos |>
ggplot(aes(x = DAP,
y = Biomasa)) +
geom_point() +
geom_line()
Valores estéticos (aes)
Guía para definir parámetros de aes:
- x: valores en eje x.
- y: valores en eje y.
- color: color de bordes o líneas.
- fill: relleno de barras, áreas, etc.
- group: Grupos, p.ej., para series de puntos y líneas, unir las de un mismo grupo
Otros menos usados: - size: tamaño del ícono. - linetype: tipo de línea. - alpha: transparencia. - width: ancho de la barra o columna.
Algunos tienen: - xmin, xmax - ymin, ymax.
Ahorita ya usamos x y y, veamos col y fill.
Color
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg)) +
geom_point()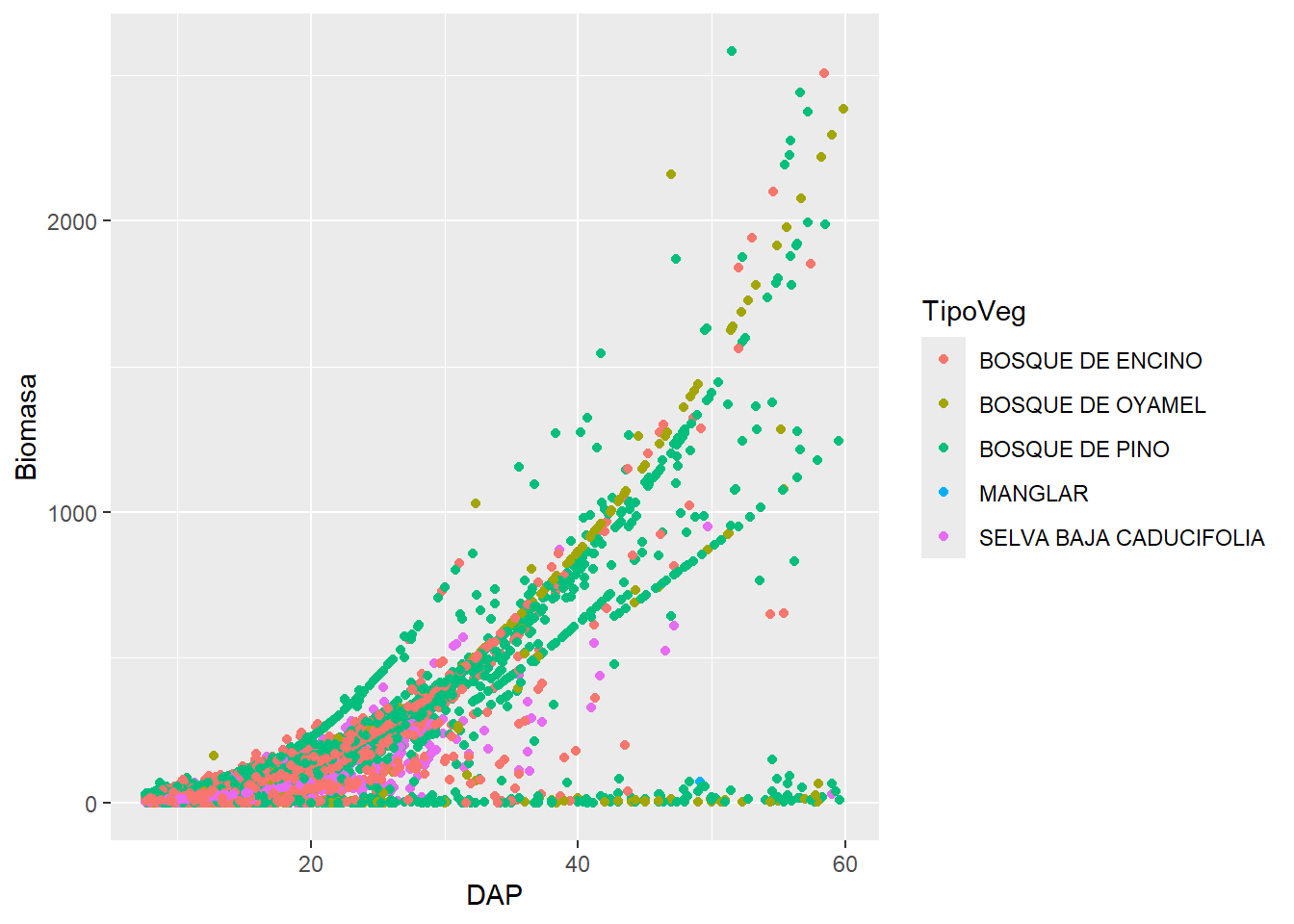
datos |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
color = Anio)) +
geom_col()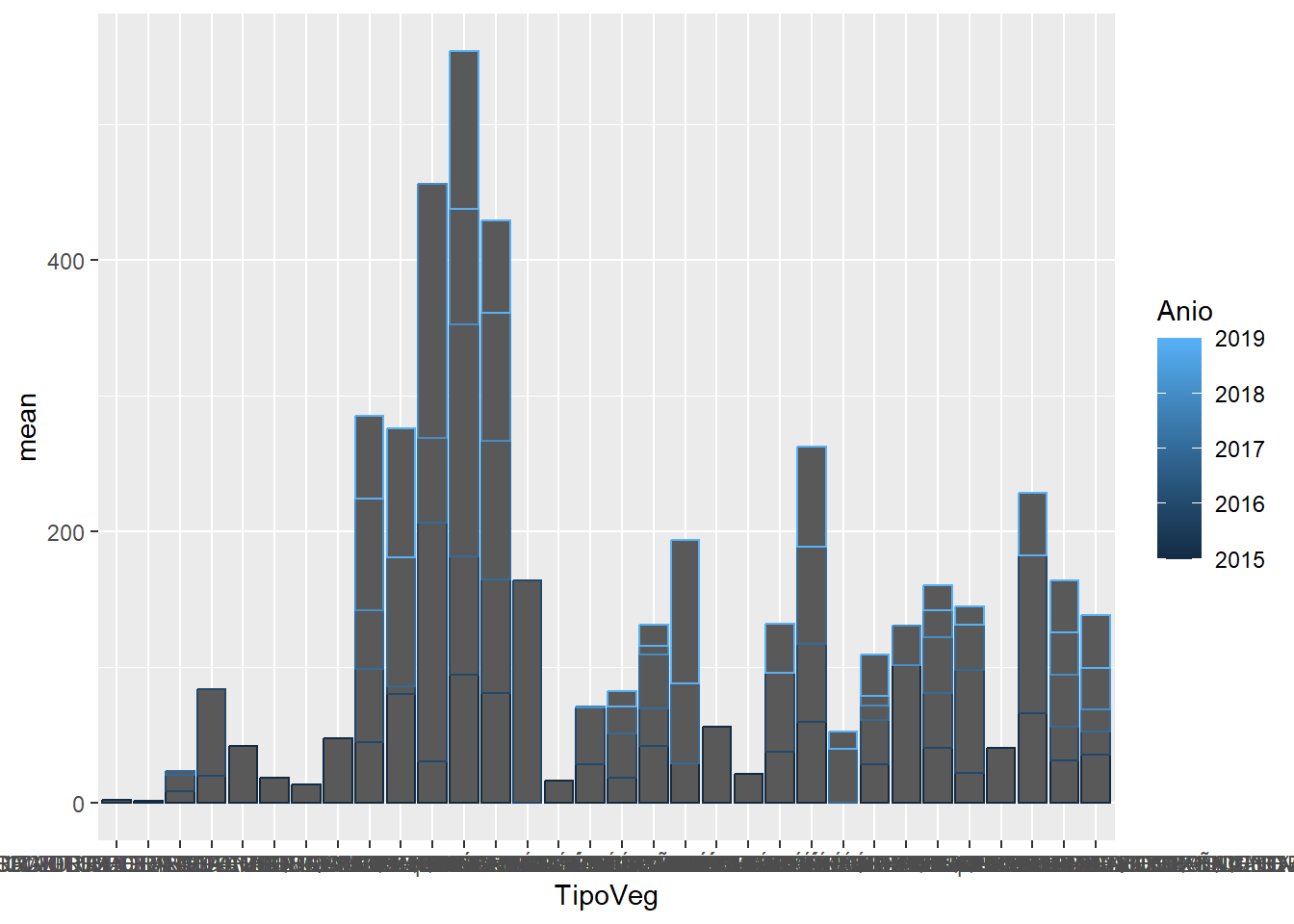
Relleno: Fill
datos |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = Anio)) +
geom_col()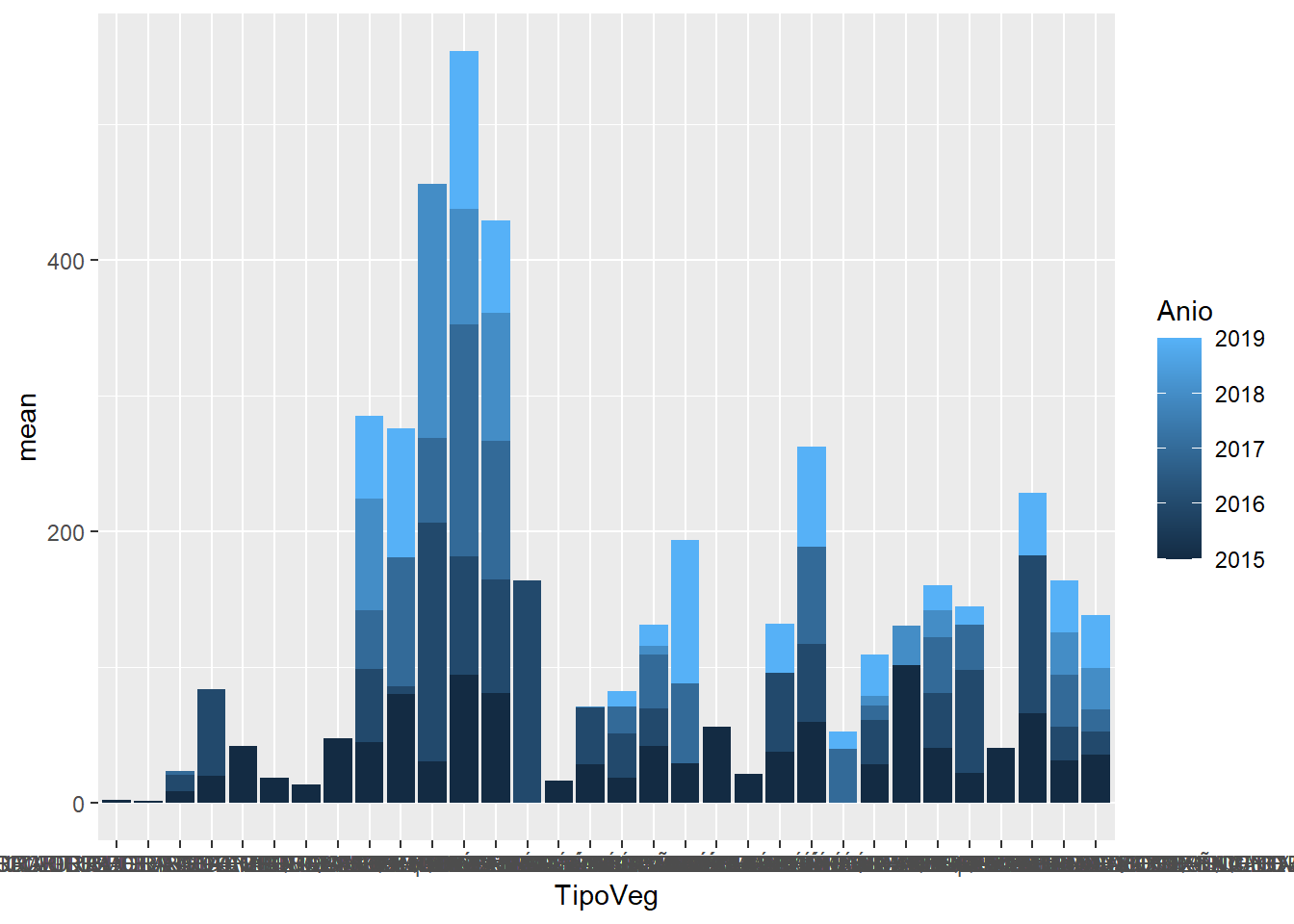
Diferencia entre numérico y factor
datos |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col()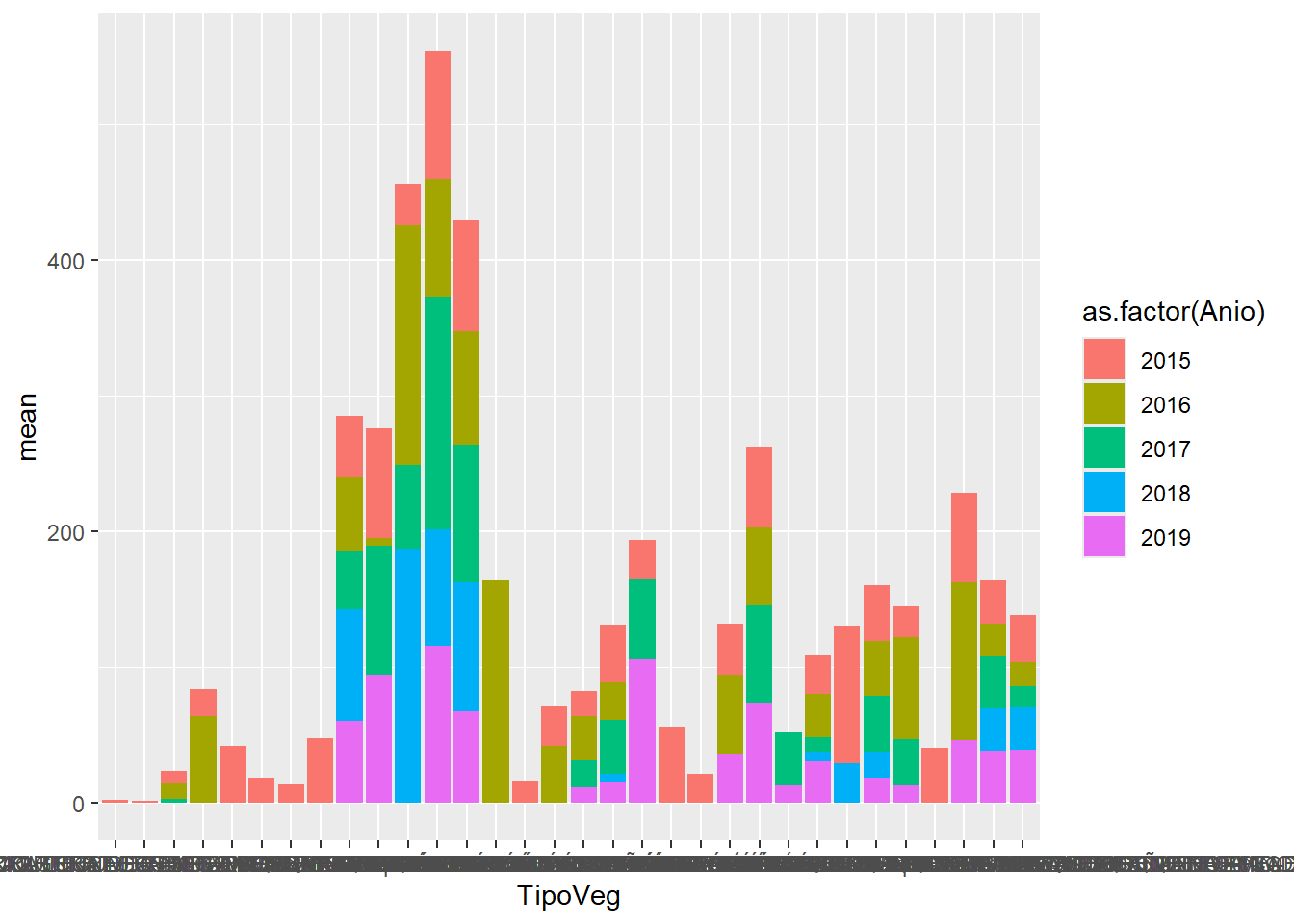
Grupos: Group
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg,
group = TipoVeg)) +
geom_line()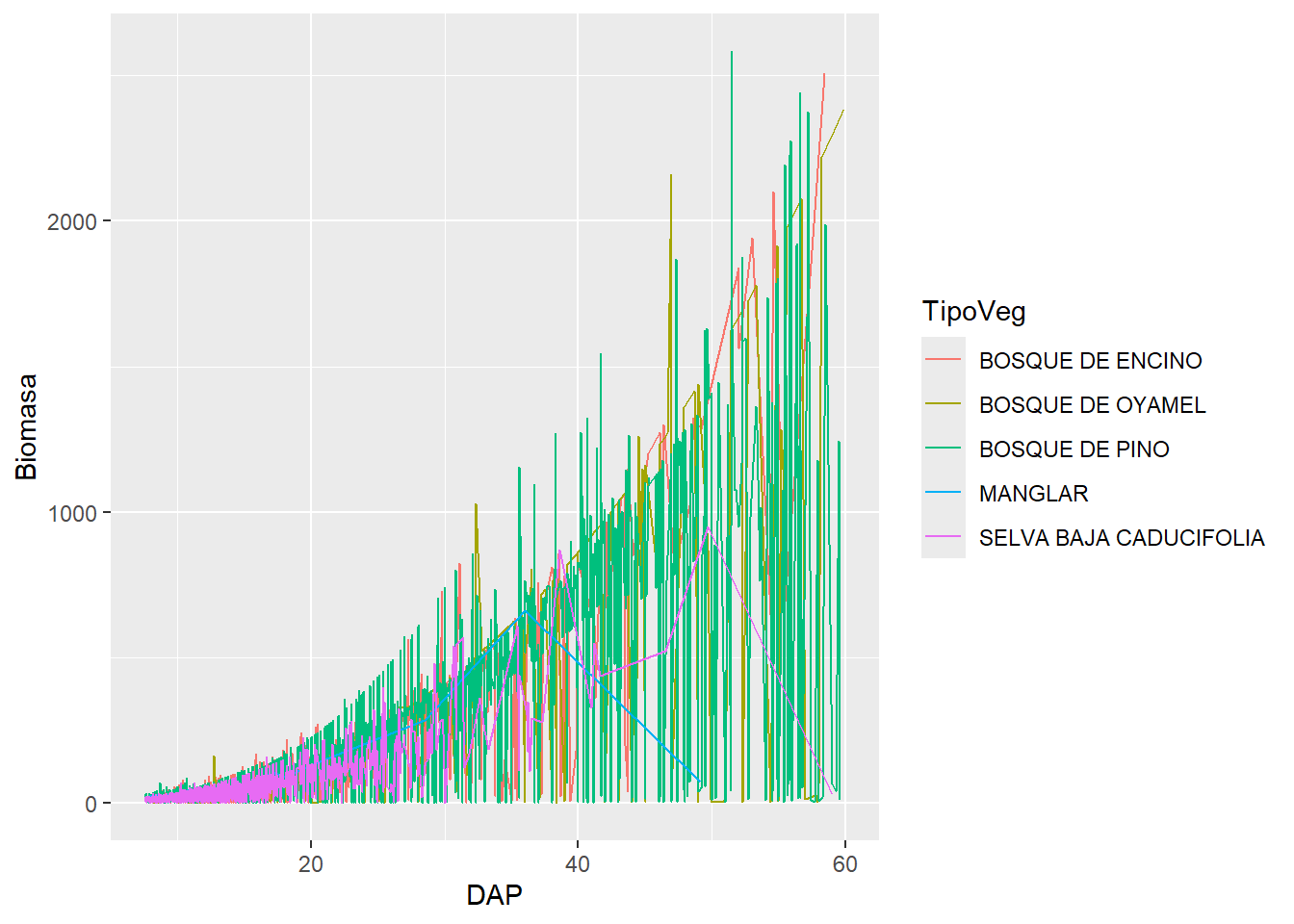
Otros
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg,
group = TipoVeg,
linetype = TipoVeg)) +
geom_line()
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg,
group = TipoVeg,
alpha = Biomasa)) +
geom_point()
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg,
group = TipoVeg,
size = Biomasa)) +
geom_point()
Posiciones para columnas
datos |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col(position = "dodge")
datos |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col(position = "stack")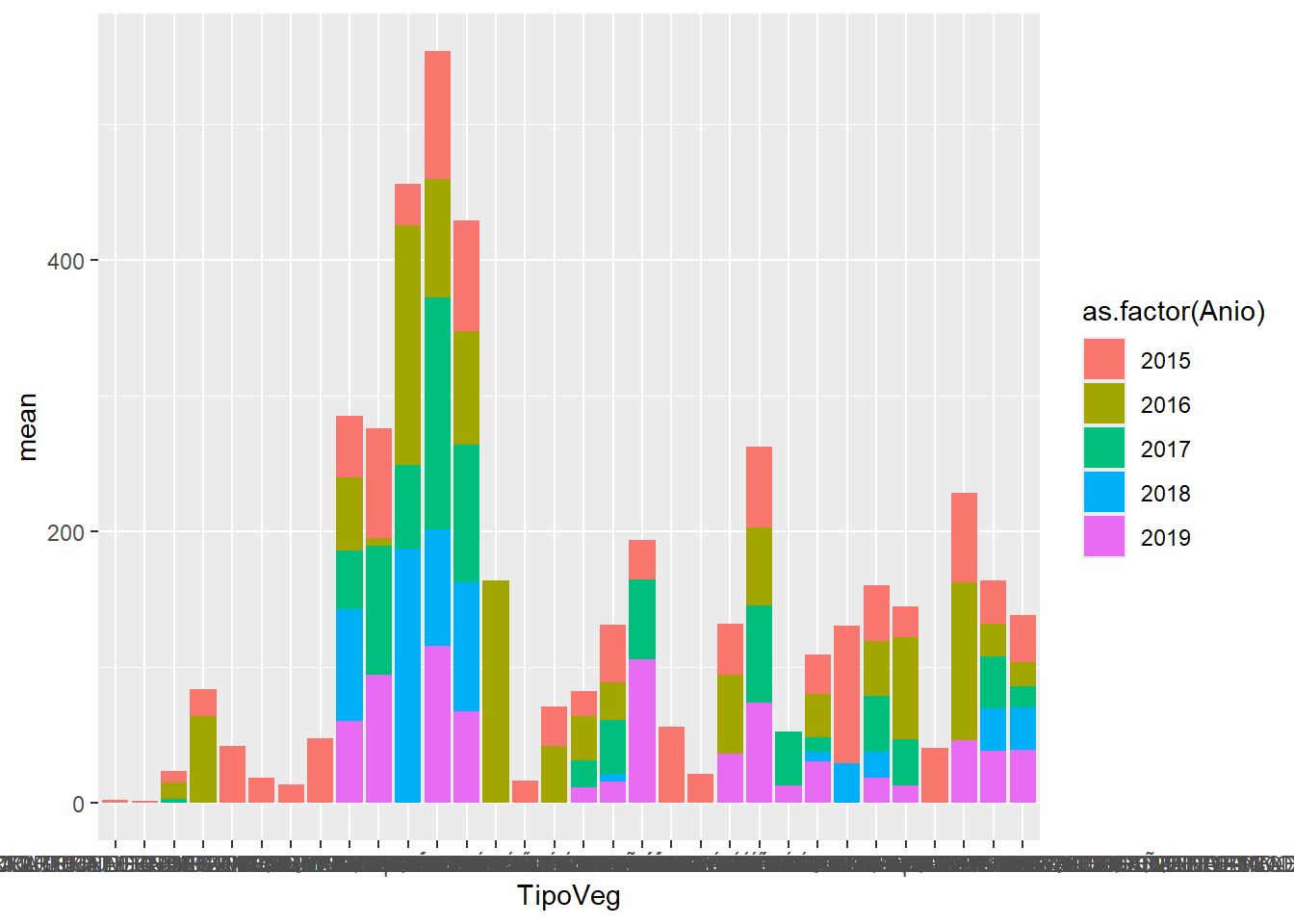
Personalización
Títulos de ejes y leyenda: labs
Aquí el truco es poner el nombre del elemento indicado en la sección de aes como título de leyenda. En el caso de varias leyendas, se pueden indicar por separado.
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg,
group = TipoVeg)) +
geom_line() +
labs(x = "Diámetro",
y = "Biomasa (kg)",
color = "Tipo de Vegetación")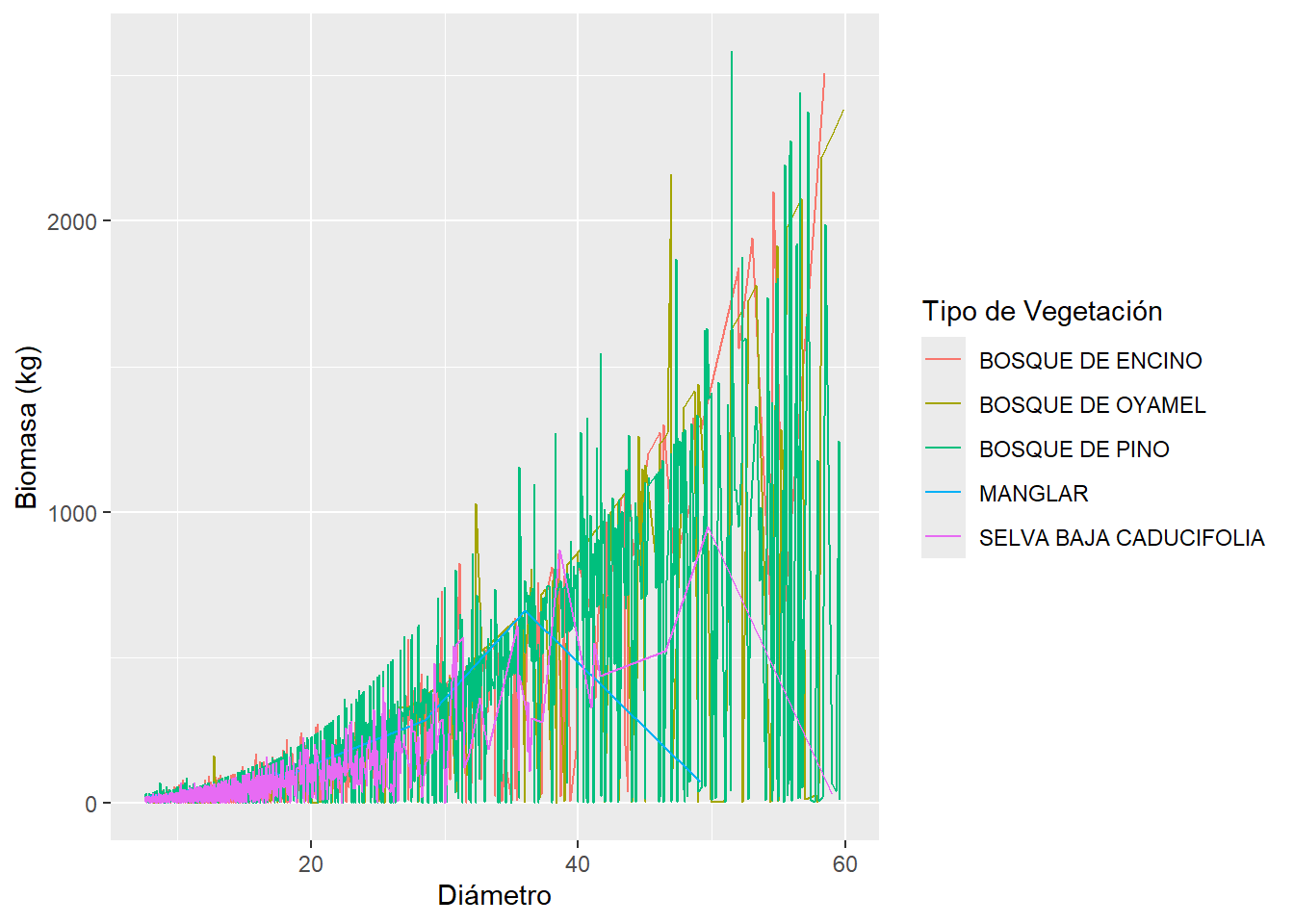
Modificar escalas de ejes: scales
- Scale_x
- _continuous: cuando la variable es numérica.
- _discrete: cuando la variable es discreta (factor).
- Scale_y
- _continuous: cuando la variable es numérica.
- _discrete: cuando la variable es discreta (factor).
Parámetros importantes:
- breaks: intervalos con etiqueta.
- limits: límites del gráfico.
- expand: qué tanto espacio se deja entre los ejes y la primera observación.
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg,
group = TipoVeg)) +
geom_line() +
scale_x_continuous(breaks = seq(0,250,25),
limits = c(0,250),
expand = c(0,0))+
scale_y_continuous(breaks = seq(0,10000,1250),
limits = c(0,10000),
expand = c(0,0))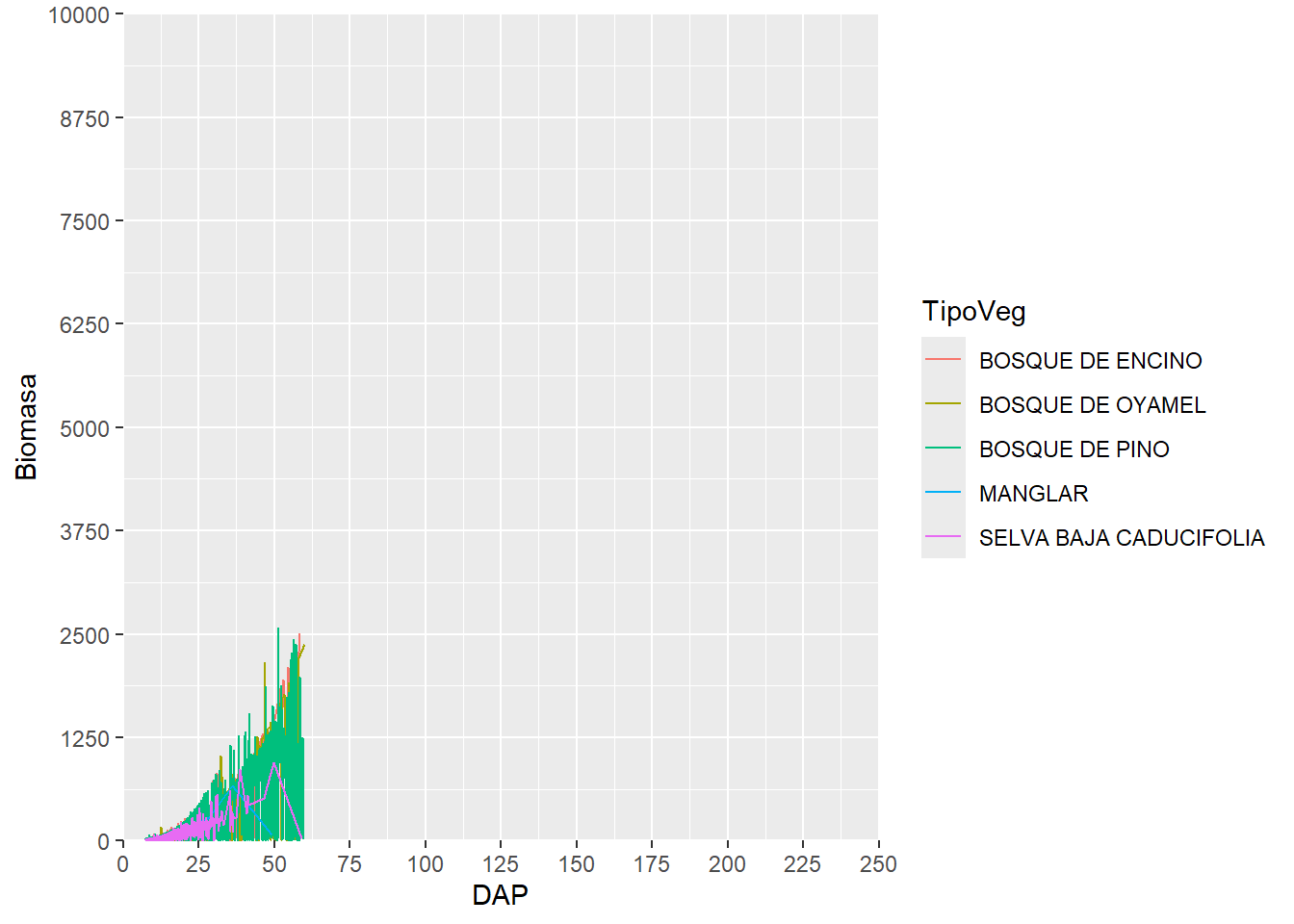
Ejes discretos
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
mutate(across(TipoVeg, ~as.factor(.x))) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() 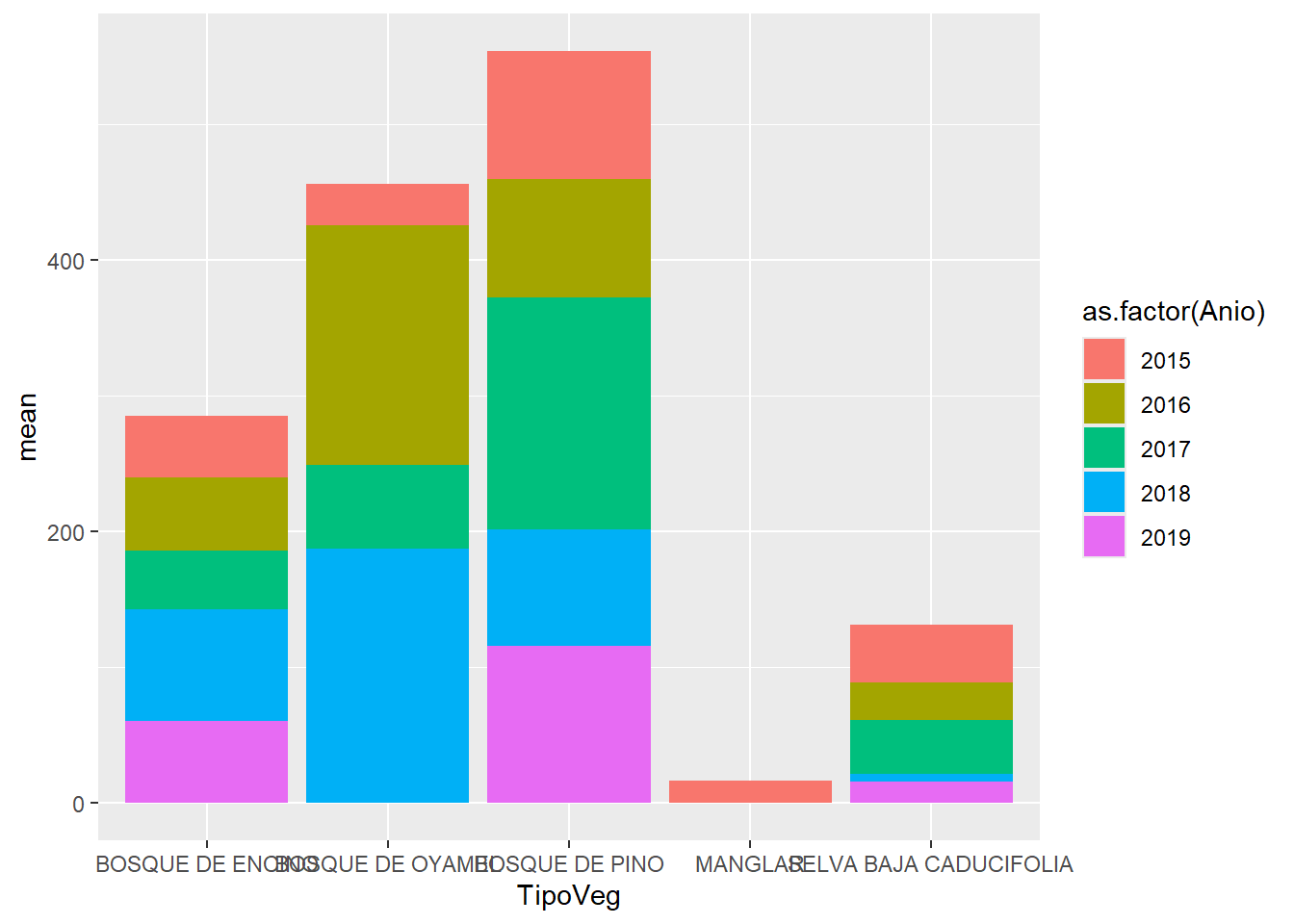
Por default ejes discretos los pone en orden alfabético. Para cambiar el orden.
Ejes discretos
Opción 1: Cambiar orden de factores
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
mutate(across(TipoVeg, ~factor(.x, levels = c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")))) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
scale_x_discrete(labels = c( "Selva Baja Caducifolia", "Bosque de Pino", "Bosque de Encino", "Bosque de Oyamel", "Manglar"))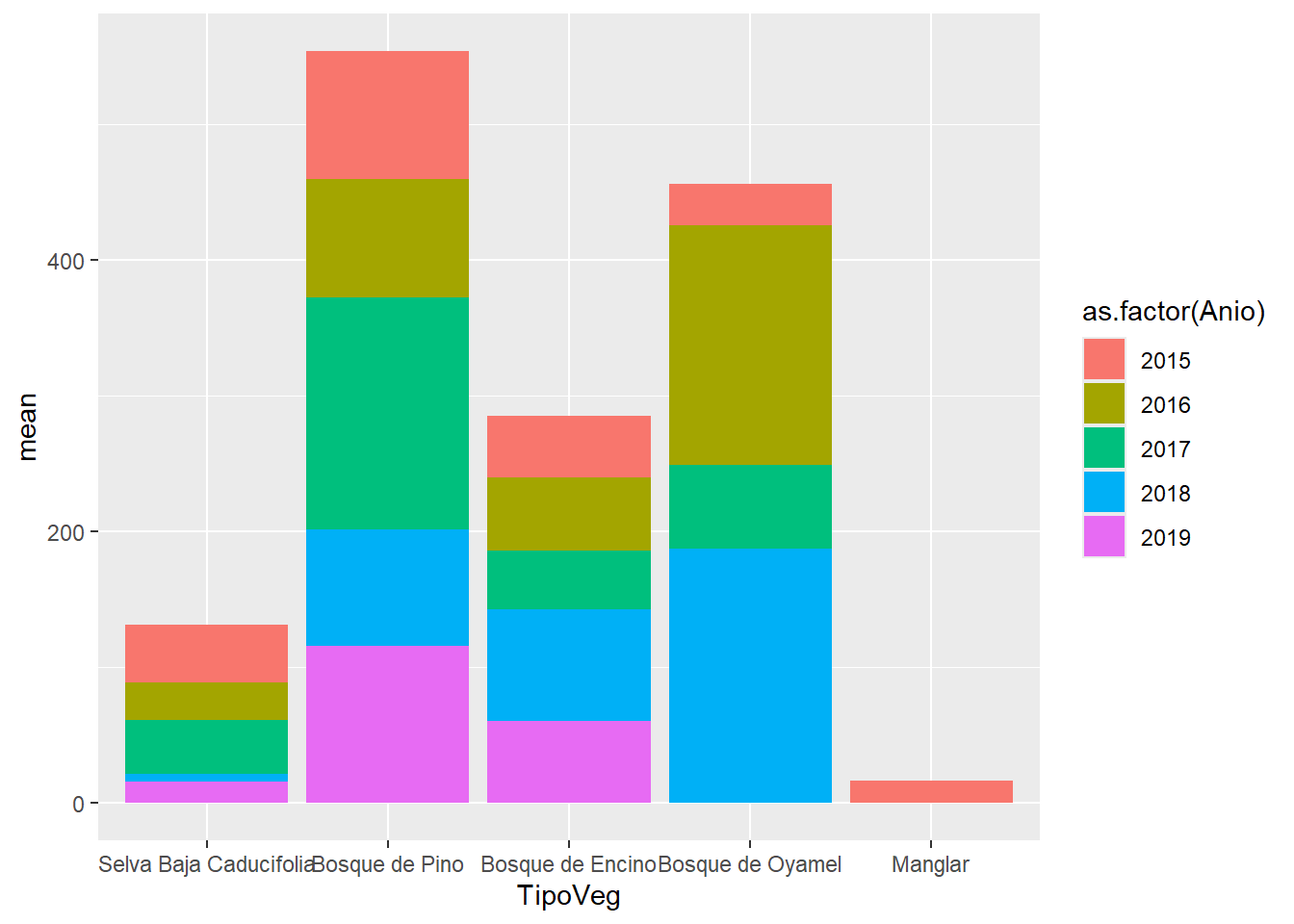
Opción 2: Poner límites
datos_sub <- datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
mutate(across(TipoVeg, ~as.factor(.x)))
datos_sub |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
scale_x_discrete(limits = rev(levels(datos_sub$TipoVeg)))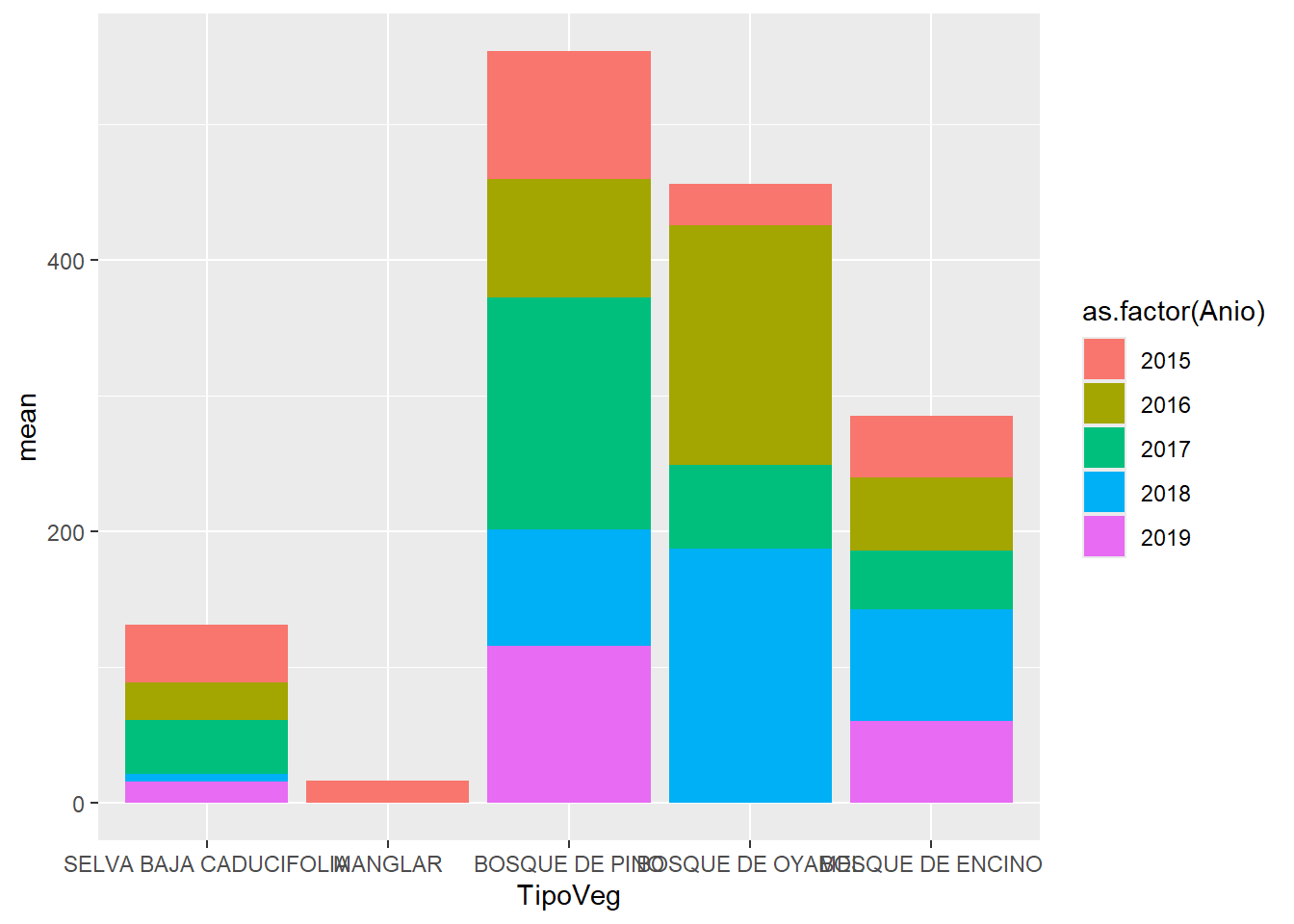
Cambiar colores por default: Scale_fill/col
- scale_fill
- _manual
- _continuous: continuos.
- _discrete: discretos.
- _brewer: discretos.
- _distiller: continuos.
- scale_color
- _manual
- _continuous: continuos.
- _discrete: discretos.
- _brewer: discretos.
- _distiller: continuos.
Revisar paletas de colores de ggplot2 y colores hexadecimales:
Otro paquete muy útil para crear paletas: RColorBrewer.
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
scale_fill_brewer(palette = "PuBuGn")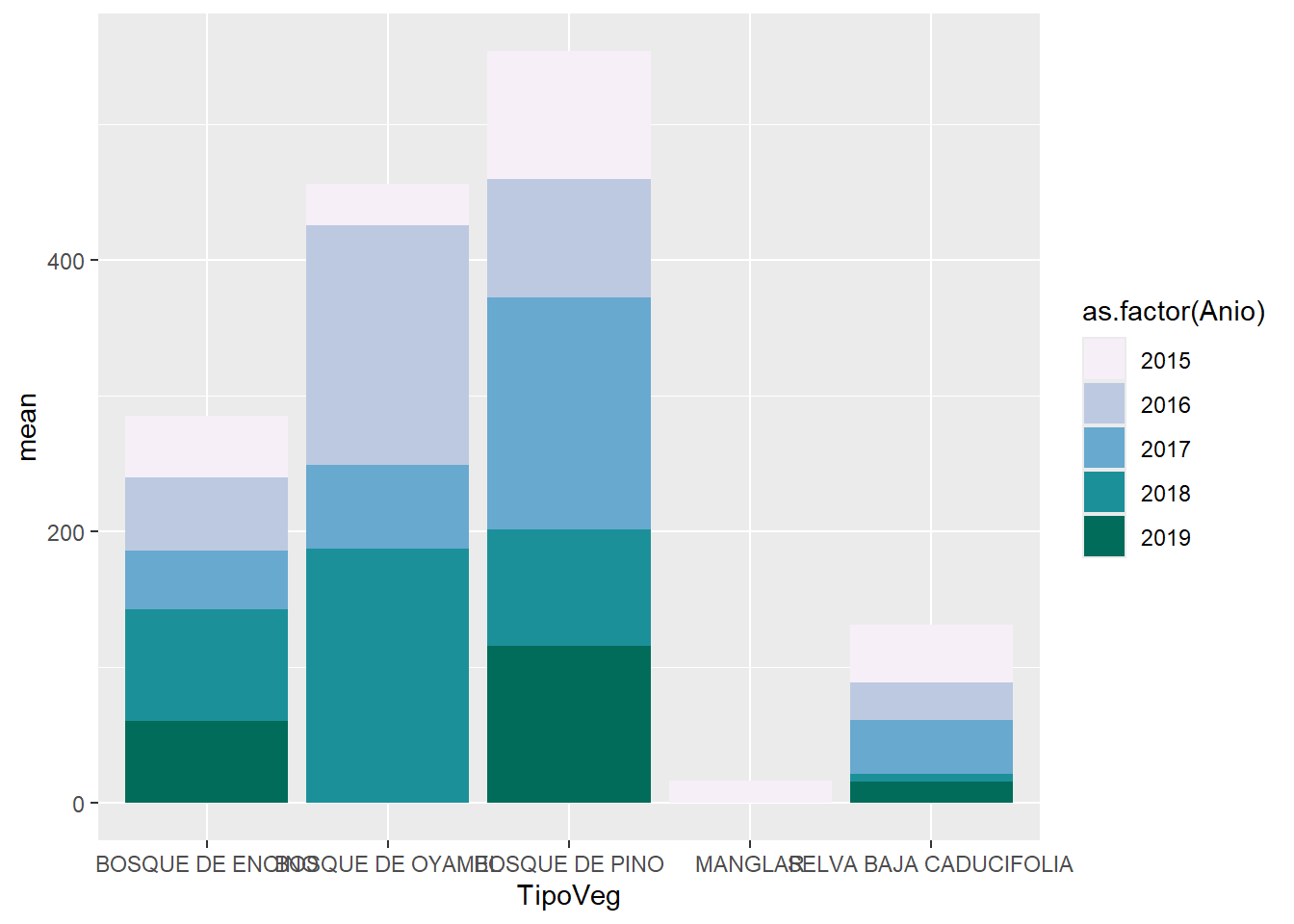
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
scale_fill_manual(values = c("forestgreen","yellow2", "orange1", "red1", "royalblue"))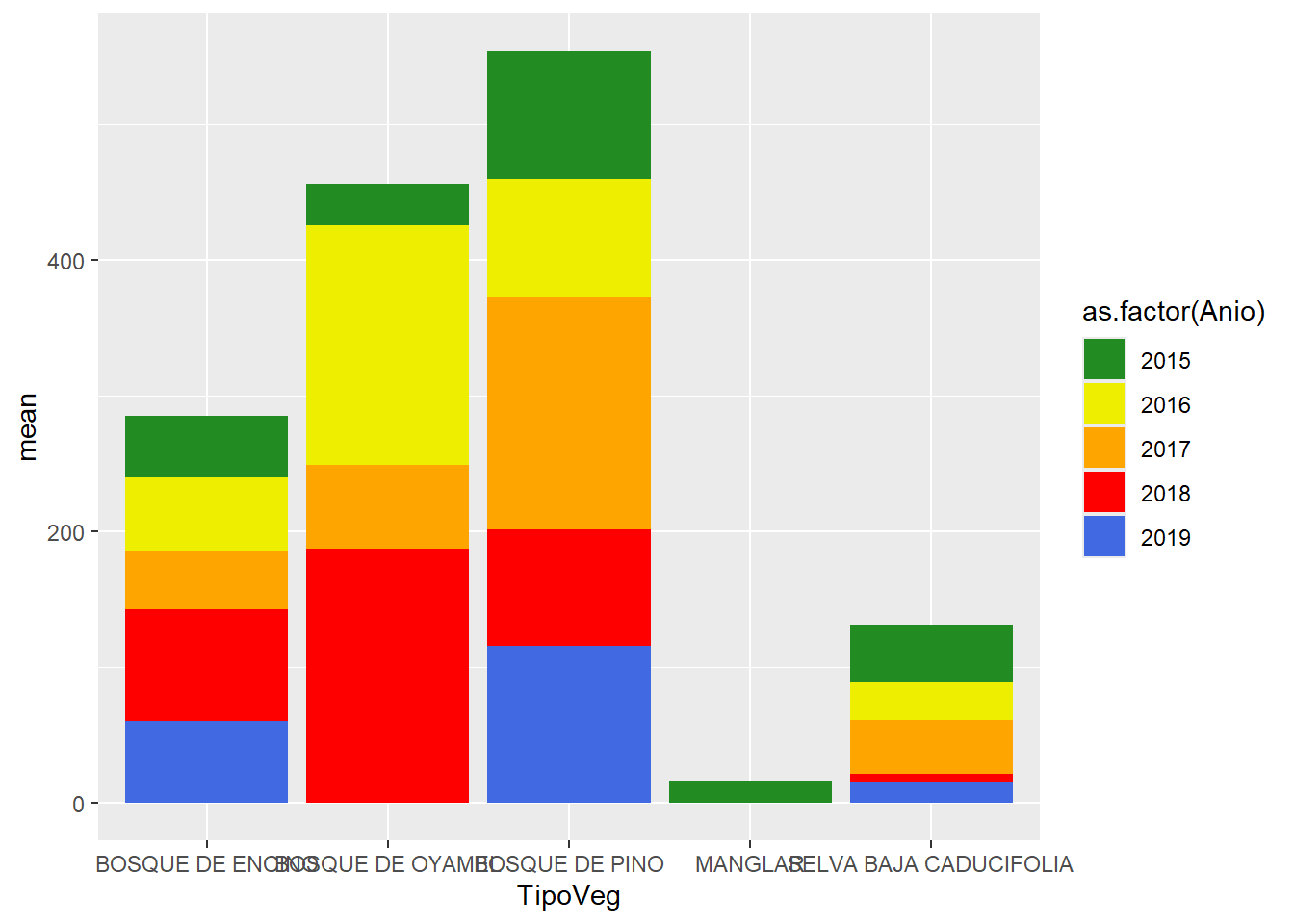
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
scale_fill_manual(values = RColorBrewer::brewer.pal(5, "Accent"))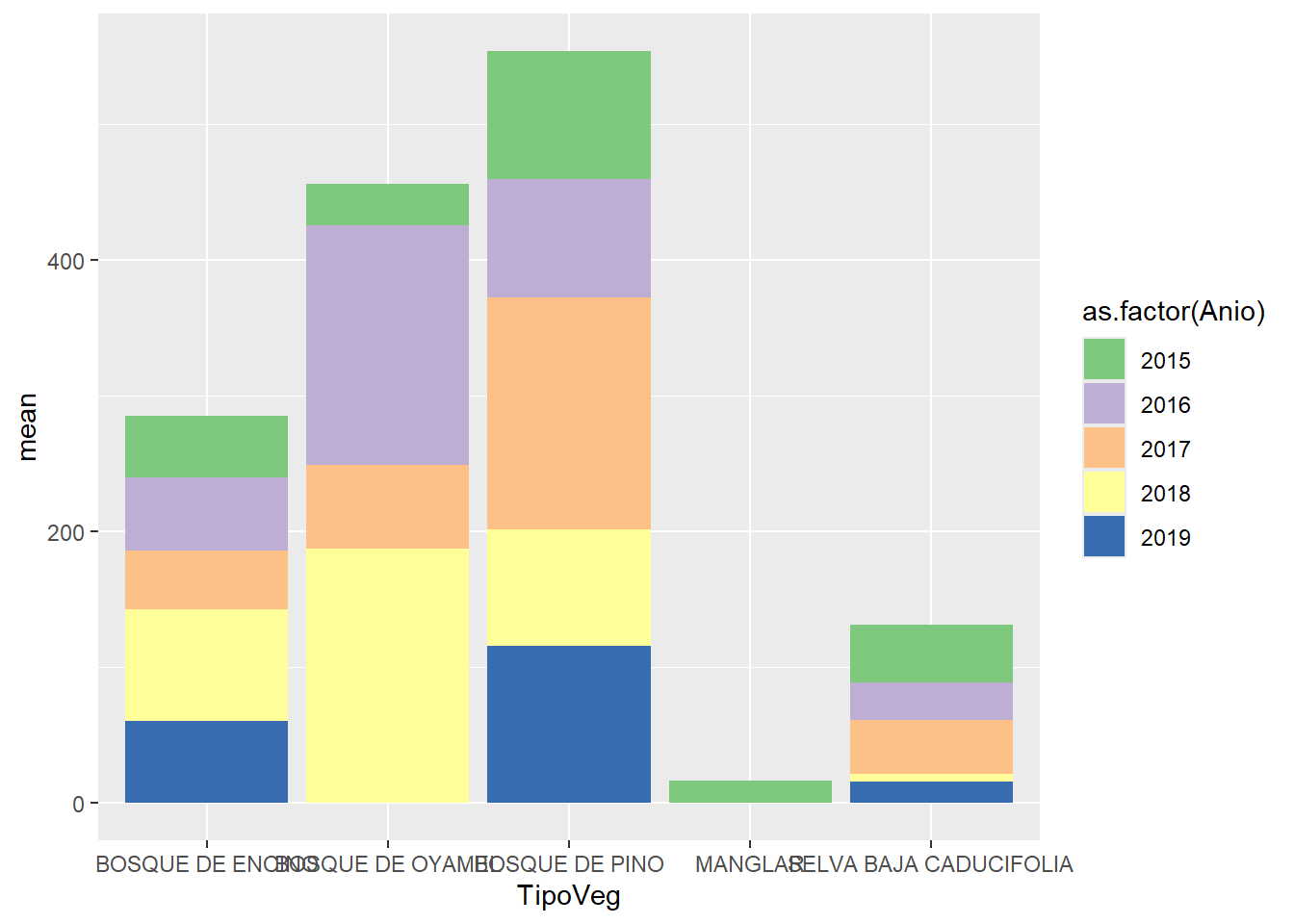
Facets
Facet_wrap
Hacer gráficos de varios paneles. Los argumentos más relevantes son:
- Fórmula que indica los paneles.
- Número de columnas o filas.
- Si las escalas varían en x (“free_y”), y (“free_y”), ambas (“both”) o ninguna.
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
facet_wrap(~ as.factor(Anio),
ncol = 3,
scales = "free_y")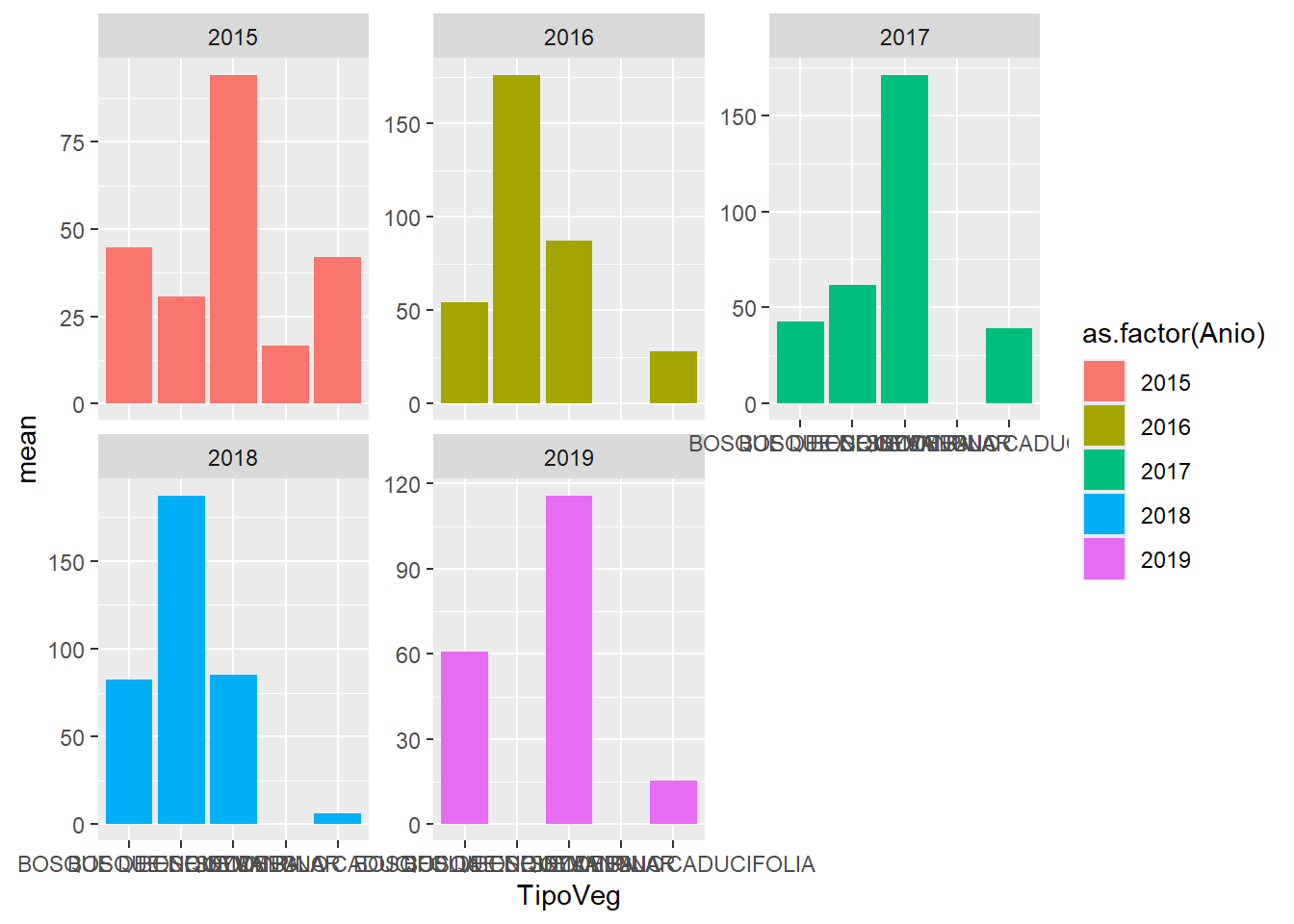
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
facet_wrap(~ as.factor(Anio),
ncol = 3,
scales = "free_x")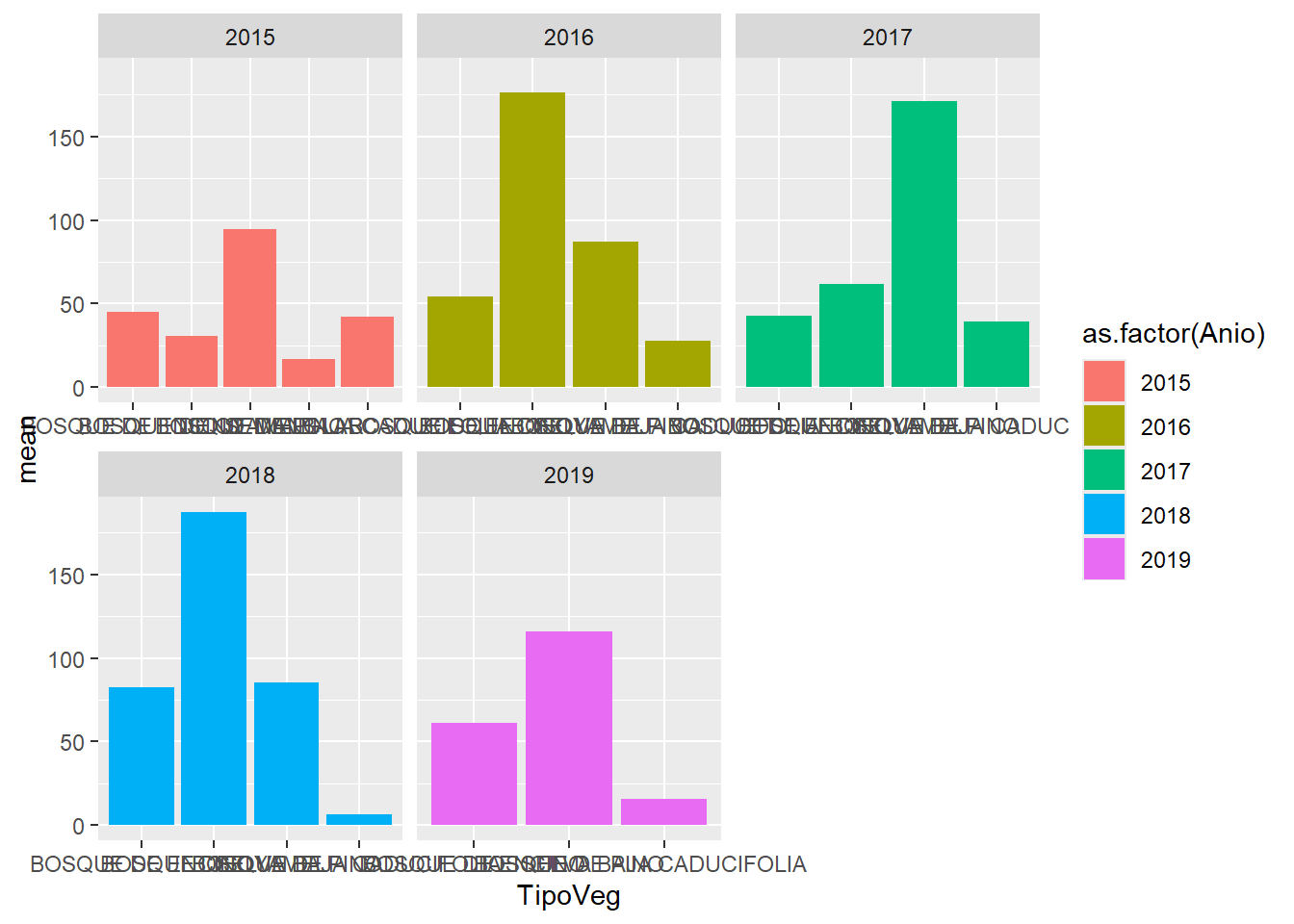
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
facet_wrap(~ as.factor(Anio),
ncol = 3,
scales = "free")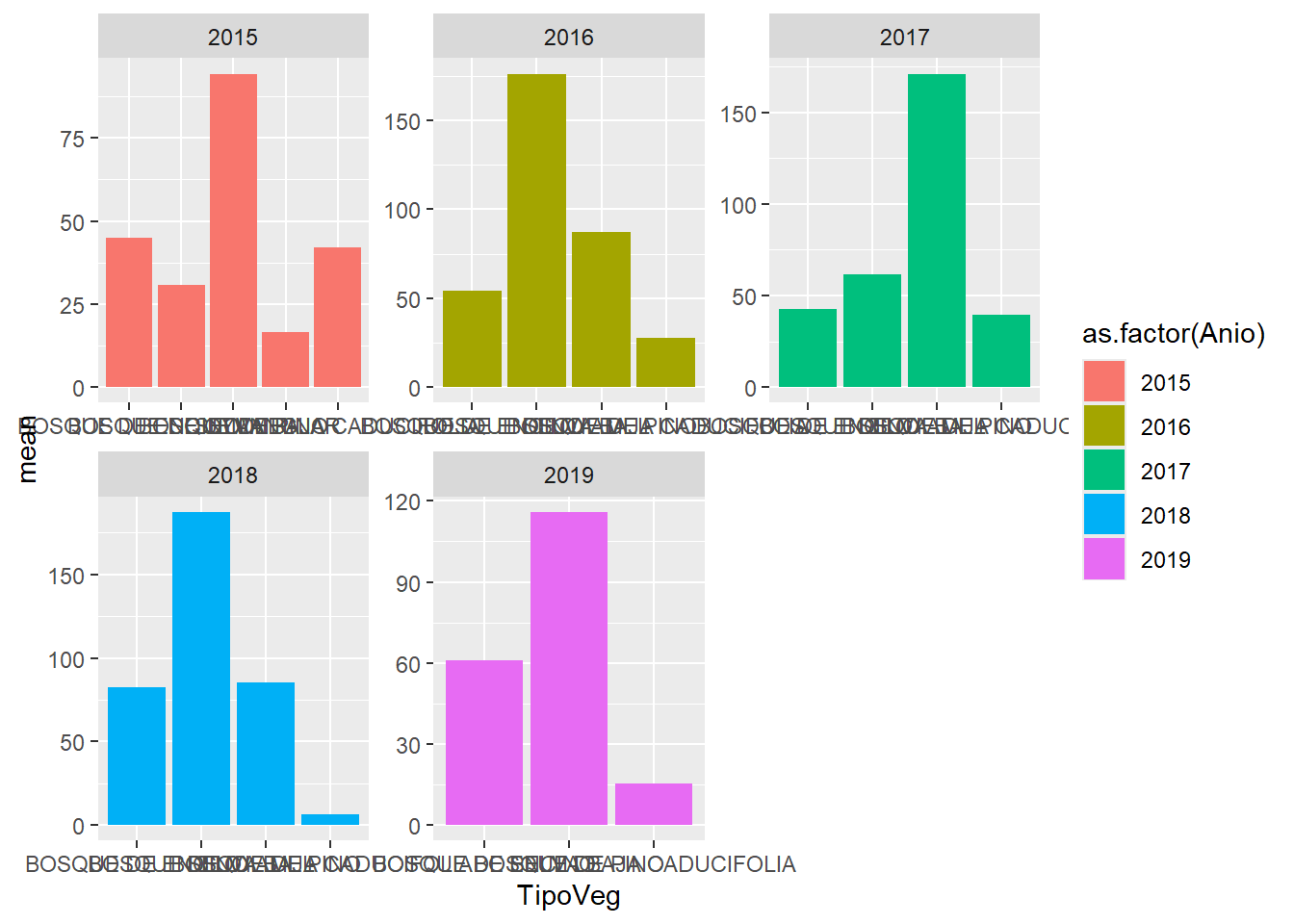
Facet_grid
Hacer gráficos de varios paneles, con una cuadrícula de dos factores
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(Ecorregion, TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(Ecorregion, TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
facet_grid(as.factor(Ecorregion) ~ as.factor(Anio),
scales = "free_y")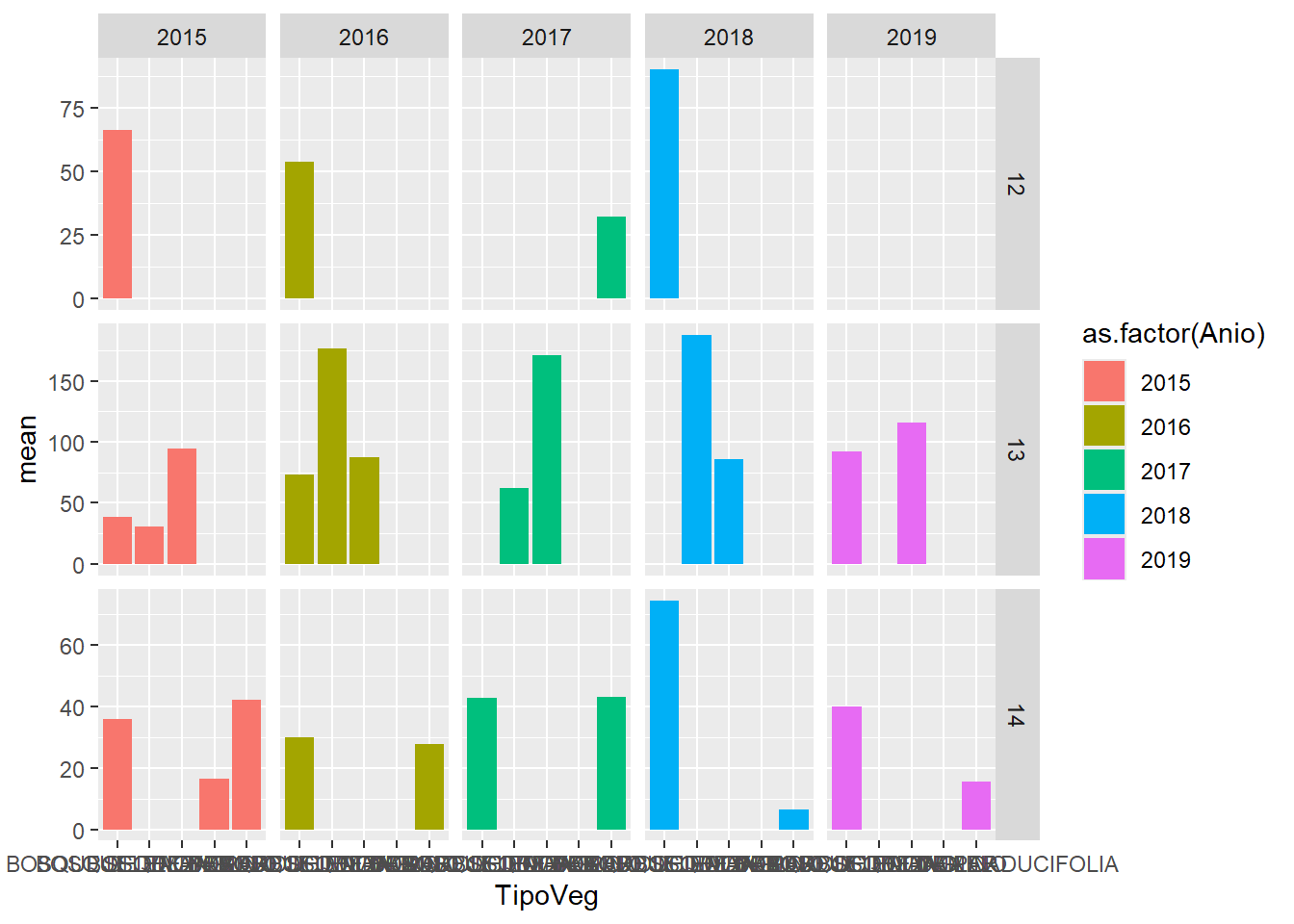
Comparado con facet_wrap que genera títulos de paneles combinados.
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(Ecorregion, TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(Ecorregion, TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = as.factor(Anio))) +
geom_col() +
facet_wrap(as.factor(Ecorregion) ~ as.factor(Anio),
scales = "free_y")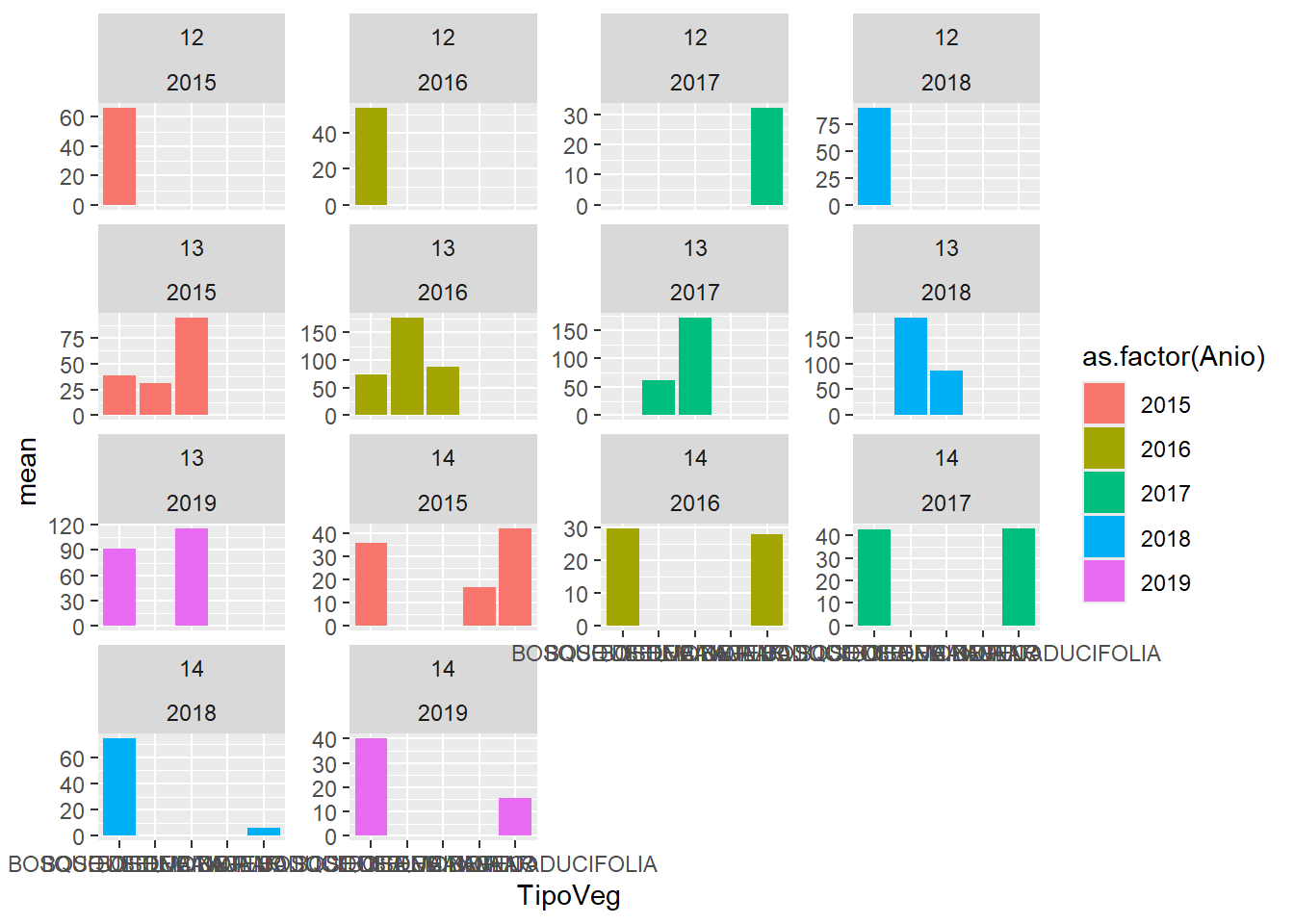
Modificar tema
Temas prediseñados
- theme_bw
- theme_gray
- theme_dark
- theme_void
- theme_minimal
- cowplot::theme_cowplot
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme_bw()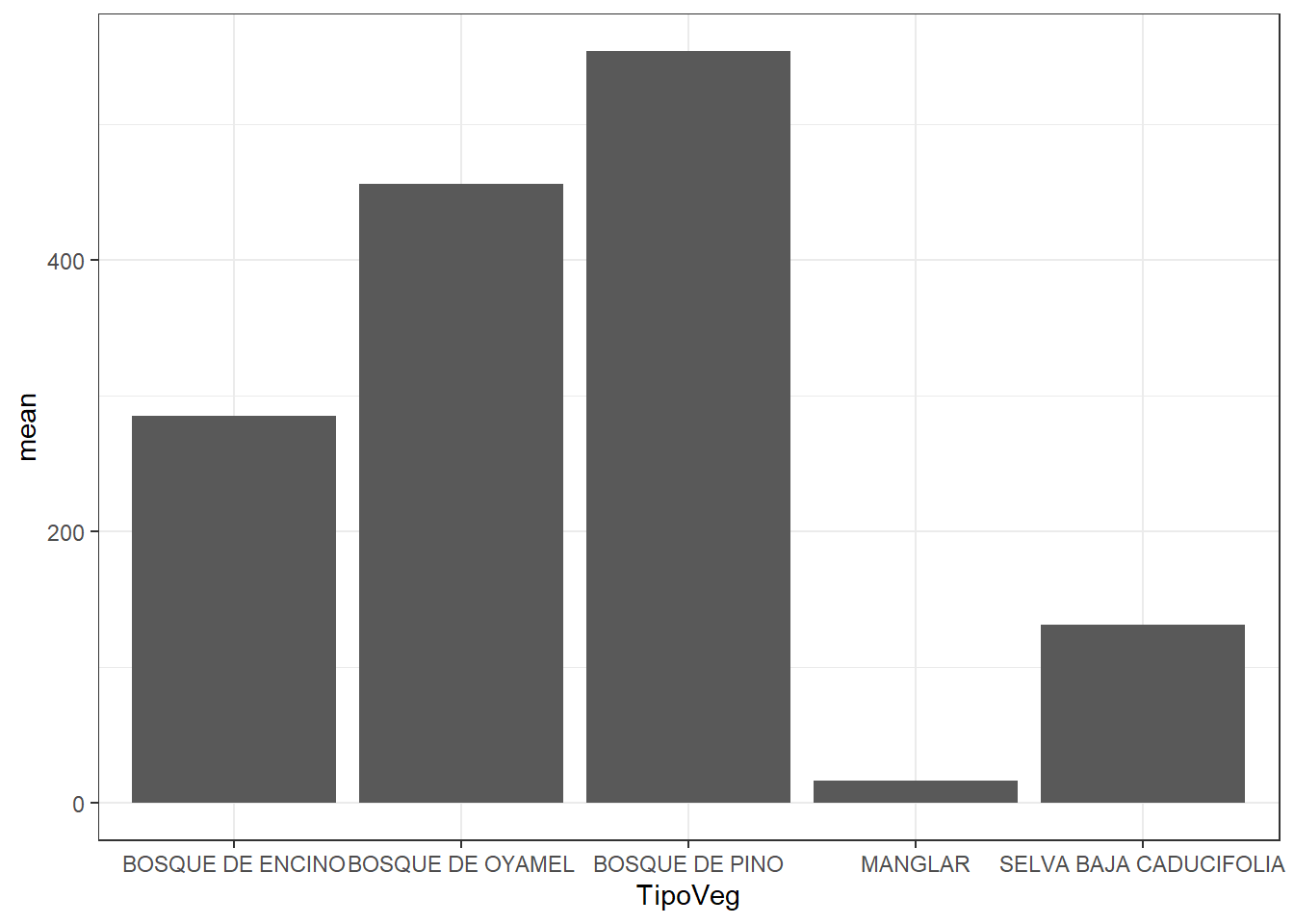
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme_gray()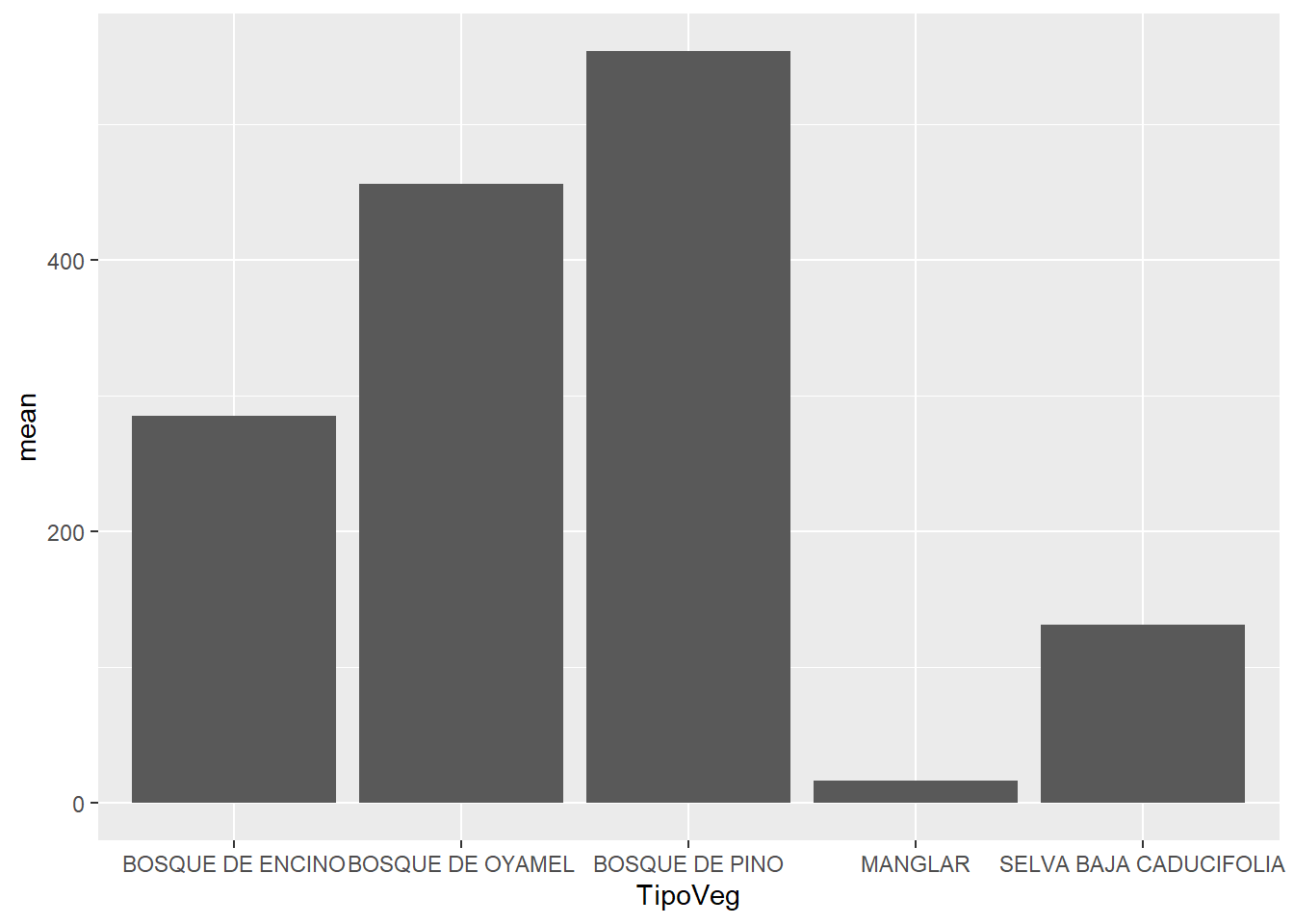
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme_dark()
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme_minimal()
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme_void()
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
cowplot::theme_cowplot()
Personalizar tema
Opciones de tema tenemos opciones sobre:
- Ejes.
- Títulos de ejes.
- Texto de ejes.
- Marcas de ejes.
- Leyenda.
- Texto.
- Fondo.
- Borde.
- Panel.
- Fondo.
- Divisiones menores y mayores.
- Área de gráfica.
- Título.
- Fondo.
- Tiras (Strip)
- Texto.
- Fondo.
Ejemplo
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme(plot.title = element_text(size=18,hjust = 0.5),
text = element_text(size=14,colour="black"),
axis.text.x = element_text(size=10,
colour="black",
angle = 90,
hjust = 1,
vjust = 0.5),
axis.text.y = element_text(size=10,
colour="black",
angle = 0,
vjust = 0.5,
hjust = 1),
axis.title = element_text(size=16,
colour="black",
face = "bold"),
axis.line = element_line(colour = "black"),
legend.title = element_text(size=18),
legend.text = element_text(size=18),
axis.line.x = element_line(colour="black"),
axis.line.y = element_line(colour="black"),
panel.grid.major = element_blank(),
panel.grid.minor = element_blank(),
panel.border = element_blank(),
panel.background = element_blank(),
strip.background = element_rect(fill="gray90",
colour = "black"),
strip.text = element_text(size=18,
colour="black",
face = "bold"),
plot.margin = unit(c(0.01,0.01,0.01,0.01), "cm"))
Opciones para elementos de theme
- element_blank. Elemento en blanco.
- element_line. Elemento de tipo línea.
- element_rect. Elemento de tipo rectángulo.
- element_text. Elemento de tipo texto.
Cambiar color de fondo
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col() +
theme(axis.text.x = element_text(angle = 90,
hjust = 1),
panel.background = element_rect(fill = "#156047"))
Modificaciones sin mapeo
Se pueden colocar valores únicos para cada aspecto estético de las gráficas.
Por ejemplo:
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col(fill = "#A45321",
alpha = 0.8,
width = 0.6) +
theme(plot.title = element_text(size=18,hjust = 0.5),
text = element_text(size=14,colour="black"),
axis.text.x = element_text(size=10,
colour="black",
angle = 90,
hjust = 1,
vjust = 0.5),
axis.text.y = element_text(size=10,
colour="black",
angle = 0,
vjust = 0.5,
hjust = 1),
axis.title = element_text(size=16,
colour="black",
face = "bold"),
axis.line = element_line(colour = "black"),
legend.title = element_text(size=18),
legend.text = element_text(size=18),
axis.line.x = element_line(colour="black"),
axis.line.y = element_line(colour="black"),
panel.grid.major = element_blank(),
panel.grid.minor = element_blank(),
panel.border = element_blank(),
panel.background = element_blank(),
strip.background = element_rect(fill="gray90",
colour = "black"),
strip.text = element_text(size=18,
colour="black",
face = "bold"),
plot.margin = unit(c(0.01,0.01,0.01,0.01), "cm"))
Cuando se modifican los aspectos estéticos sin mapear a una variable estos tienen que ser: 1) todos iguales, es decir, poner un solo color, valor, etc, 2) o tener la misma longitud de los niveles de la variable que se está mapeando. Por ejemplo:
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
ggplot(aes(x = TipoVeg,
y = mean)) +
geom_col(fill = RColorBrewer::brewer.pal(5, "Dark2"),
alpha = 0.8,
width = 0.6) +
theme(plot.title = element_text(size=18,hjust = 0.5),
text = element_text(size=14,colour="black"),
axis.text.x = element_text(size=10,
colour="black",
angle = 90,
hjust = 1,
vjust = 0.5),
axis.text.y = element_text(size=10,
colour="black",
angle = 0,
vjust = 0.5,
hjust = 1),
axis.title = element_text(size=16,
colour="black",
face = "bold"),
axis.line = element_line(colour = "black"),
legend.title = element_text(size=18),
legend.text = element_text(size=18),
axis.line.x = element_line(colour="black"),
axis.line.y = element_line(colour="black"),
panel.grid.major = element_blank(),
panel.grid.minor = element_blank(),
panel.border = element_blank(),
panel.background = element_blank(),
strip.background = element_rect(fill="gray90",
colour = "black"),
strip.text = element_text(size=18,
colour="black",
face = "bold"),
plot.margin = unit(c(0.01,0.01,0.01,0.01), "cm"))
Si esto no ocurre, va a marcar un error. La alternativa puede ser generar nuevas variables para mapear cierto aspecto a esa variable.
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
mutate(coloreado = ifelse(TipoVeg %in% c("BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL"), "Templado", "Tropical")) |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = coloreado)) +
geom_col(alpha = 0.8,
width = 0.6) +
scale_fill_manual(values = c("forestgreen", "purple2")) +
theme(plot.title = element_text(size=18,hjust = 0.5),
text = element_text(size=14,colour="black"),
axis.text.x = element_text(size=10,
colour="black",
angle = 90,
hjust = 1,
vjust = 0.5),
axis.text.y = element_text(size=10,
colour="black",
angle = 0,
vjust = 0.5,
hjust = 1),
axis.title = element_text(size=16,
colour="black",
face = "bold"),
axis.line = element_line(colour = "black"),
legend.title = element_text(size=18),
legend.text = element_text(size=18),
axis.line.x = element_line(colour="black"),
axis.line.y = element_line(colour="black"),
panel.grid.major = element_blank(),
panel.grid.minor = element_blank(),
panel.border = element_blank(),
panel.background = element_blank(),
strip.background = element_rect(fill="gray90",
colour = "black"),
strip.text = element_text(size=18,
colour="black",
face = "bold"),
plot.margin = unit(c(0.01,0.01,0.01,0.01), "cm"))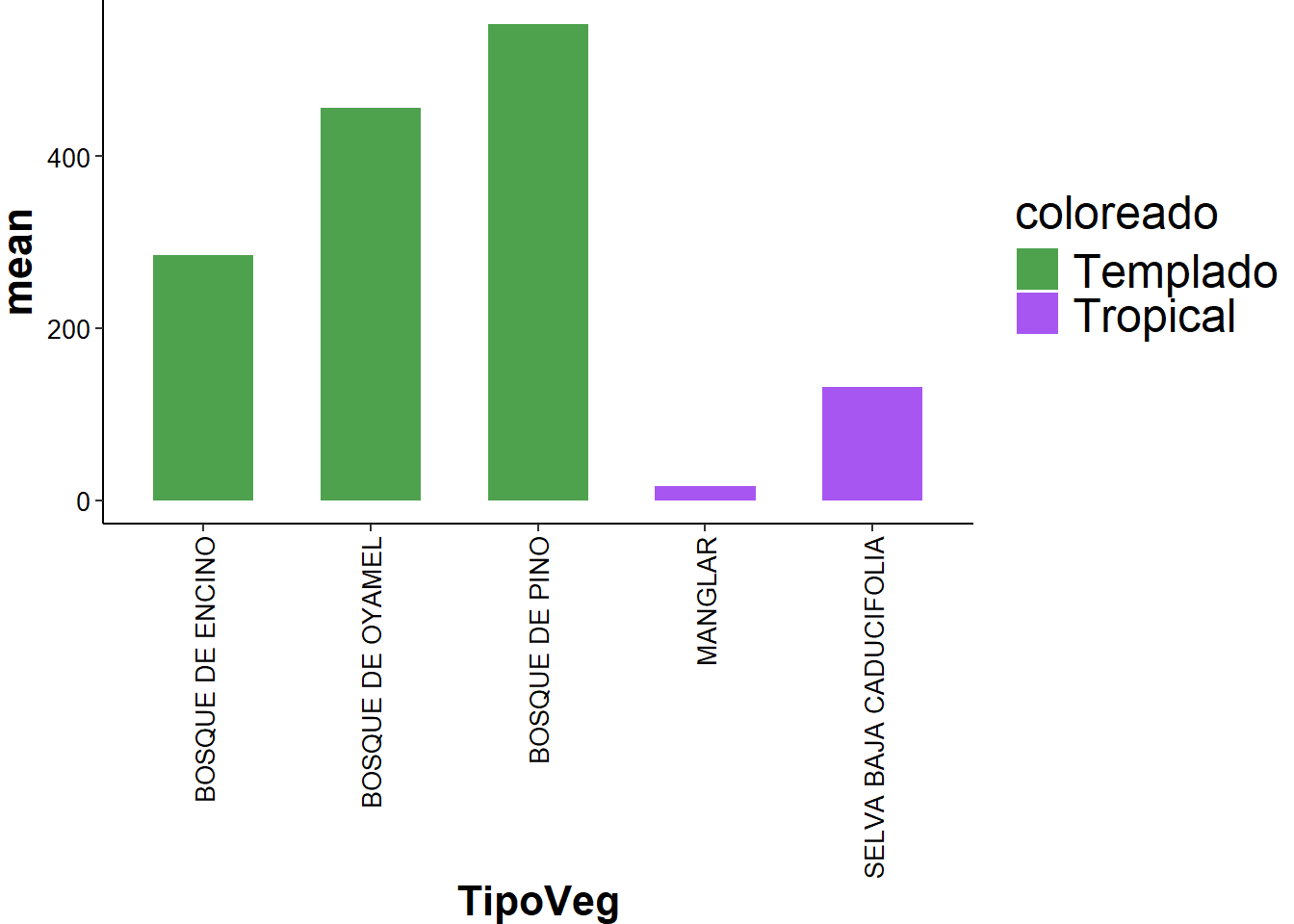
Ejemplo completo
datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
group_by(TipoVeg, Anio, ParcelaId) |>
summarise(AGB = (sum(Biomasa)/1000)*10000/1600,
.groups = "drop") |>
group_by(TipoVeg, Anio) |>
summarise(mean = mean(AGB),
.groups = "drop") |>
mutate(coloreado = ifelse(TipoVeg %in% c("BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL"), "Templado", "Tropical")) |>
ggplot(aes(x = TipoVeg,
y = mean,
fill = coloreado)) +
geom_col(alpha = 0.8,
width = 0.6) +
scale_fill_manual(values = c("forestgreen", "purple2"))+
labs(x = "Tipo de vegetación", y = "Biomasa (Mg/ha)", fill = "Tipo de bosque") +
theme(plot.title = element_text(size=18,hjust = 0.5),
text = element_text(size=14,colour="black"),
axis.text.x = element_text(size=10,
colour="black",
angle = 90,
hjust = 1,
vjust = 0.5),
axis.text.y = element_text(size=10,
colour="black",
angle = 0,
vjust = 0.5,
hjust = 1),
axis.title = element_text(size=16,
colour="black",
face = "bold"),
axis.line = element_line(colour = "black"),
legend.title = element_text(size=18),
legend.text = element_text(size=18),
axis.line.x = element_line(colour="black"),
axis.line.y = element_line(colour="black"),
panel.grid.major = element_blank(),
panel.grid.minor = element_blank(),
panel.border = element_blank(),
panel.background = element_blank(),
strip.background = element_rect(fill="gray90",
colour = "black"),
strip.text = element_text(size=18,
colour="black",
face = "bold"),
plot.margin = unit(c(0.01,0.01,0.01,0.01), "cm"))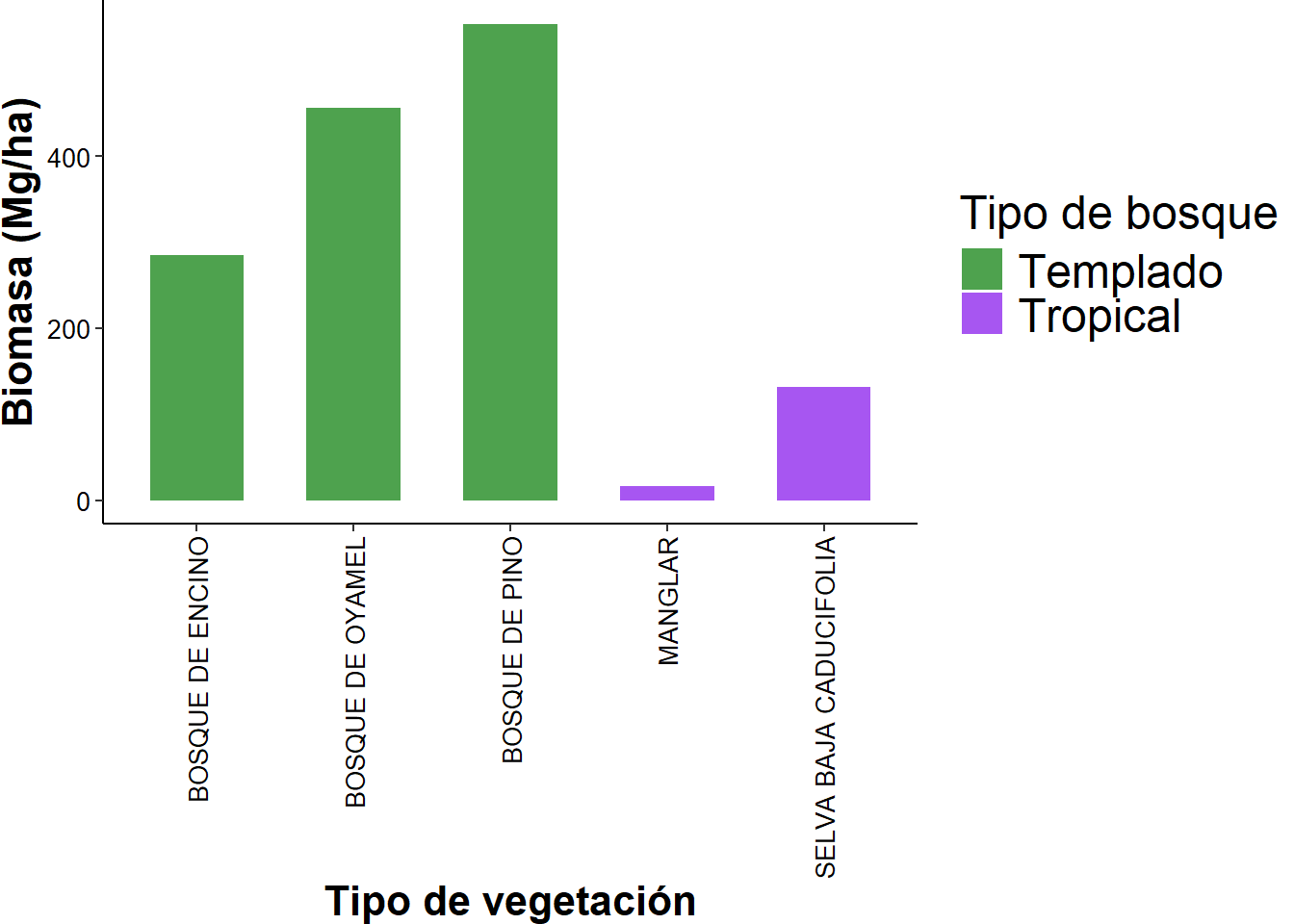
Exportar gráfico
ggsave
Guarda por default la última gráfica agregada en el panel de gráficos.
Permite guardar imágenes en formato: png, eps, ps, tex, pdatos, jpeg, tiff, bmp, svg. Si no se le indica lo toma del nombre del archivo.
ggsave(filename = "Gráfica_ggplot.jpeg",
width = 18,
height = 12,
units = "cm",
dpi = 300)Combinar más de una gráfica
Paquetes cowplot y patchwork
Cowplot
library(cowplot)
Adjuntando el paquete: 'cowplot'The following object is masked from 'package:lubridate':
stampp1 <- datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa)) +
geom_point()p2 <- datos |>
filter(TipoVeg %in% c("SELVA BAJA CADUCIFOLIA", "BOSQUE DE PINO", "BOSQUE DE ENCINO", "BOSQUE DE OYAMEL", "MANGLAR")) |>
ggplot(aes(x = DAP,
y = Biomasa,
color = TipoVeg)) +
geom_line()p3 <- plot_grid(p1,
p2,
labels = c("A", "B"),
label_size = 14)
p3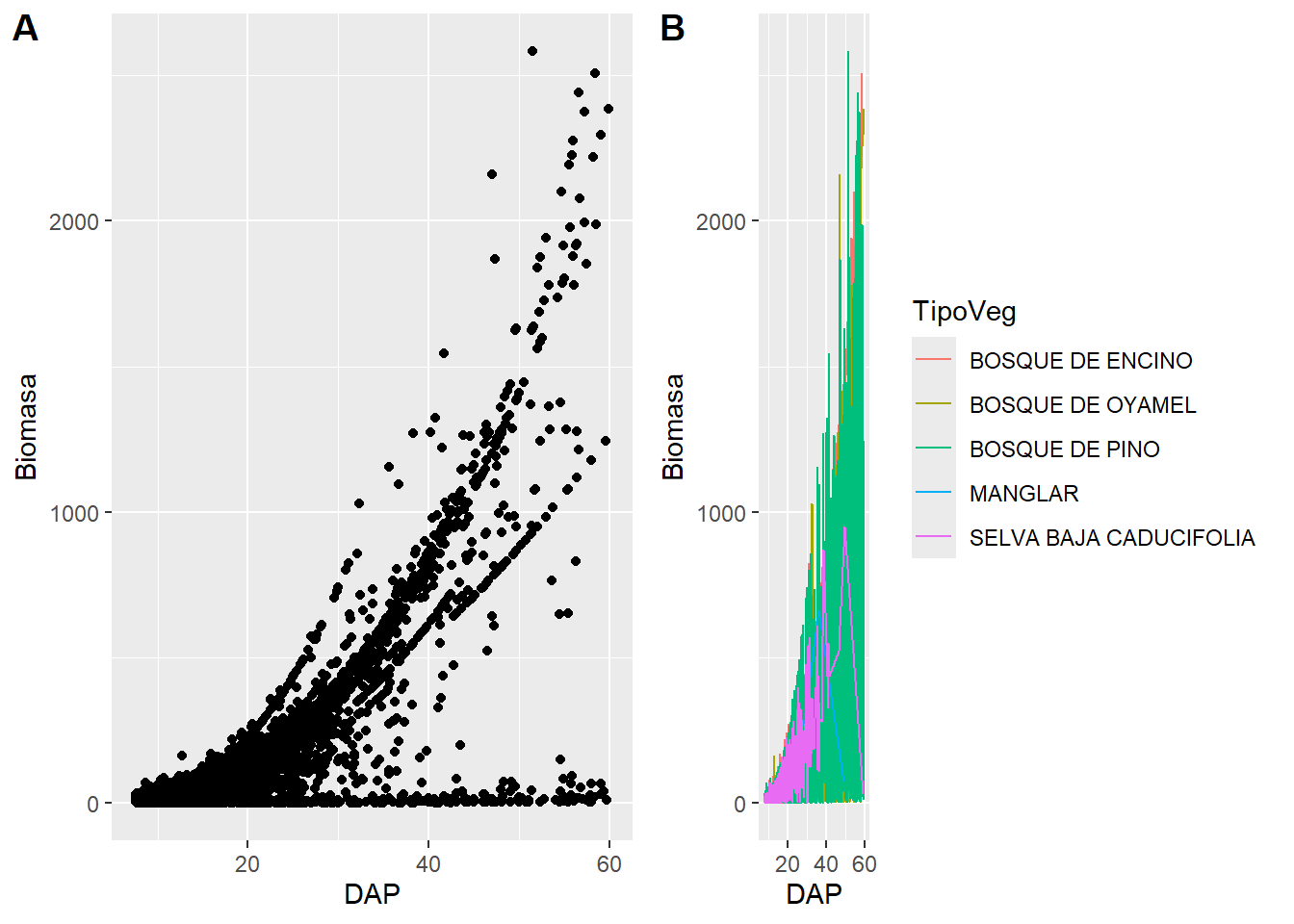
Exportar
save_plot(filename = "Gráfica_ggplot.jpeg",
plot = p3,
base_width = 18,
base_height = 12,
units = "cm",
dpi = 300)Patchwork
library(patchwork)
Adjuntando el paquete: 'patchwork'The following object is masked from 'package:cowplot':
align_plotsp1 + p2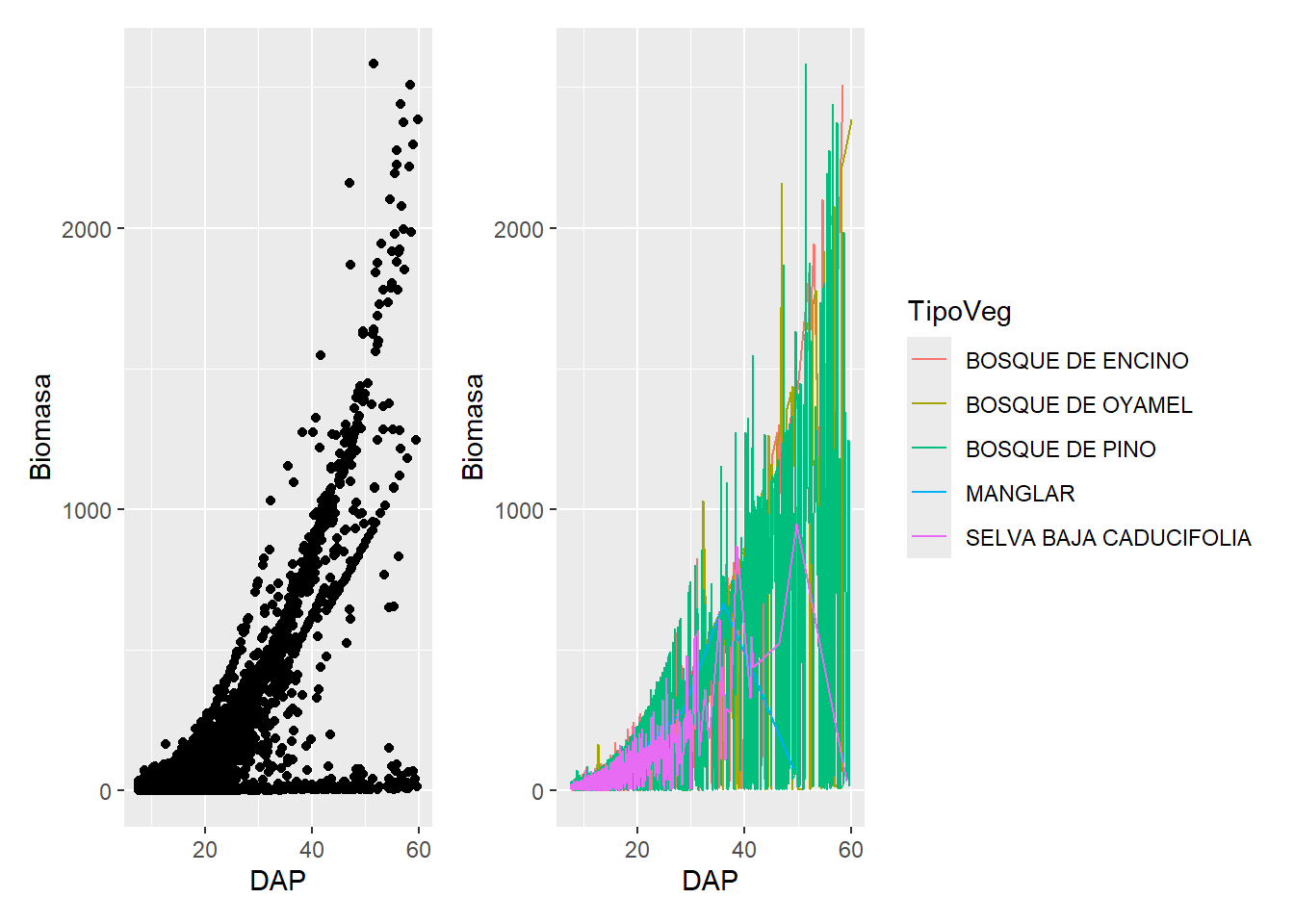
p3 <- p1 + p2p1 / p2
Exportar
ggsave(filename = "Gráfica_ggplot.jpeg",
plot = p3,
width = 18,
height = 12,
units = "cm",
dpi = 300)Otros paquetes para expander las capacidades de ggplot
- Animar gráficas: gganimate.
- Agregar datos estadísticos: ggstatsplot.
- Resalta componentes: gghighlight.
- Crear “fills” con patrones (p.ej. achurado): ggpattern.
- Evitar etiquetas sobrelapadas: ggrepel.
- Agregar texto en líneas: geomtextpath.
- Temas prehechos: ggthemes, hrbrthemes.
- Generar gráficas de nodos, treemaps, árboles: ggraph.
- Generar gráficas interactivas html: ggiraph.
- Agregar etiquetas y texto: ggtext.
- Crear gráficas de manera interactiva (minimiza el uso de código): esquisse.
- Treemaps: treemap.
- Mapas interactivos: leaflet.